Introducción
El incremento en la resistencia generada por las bacterias a los antibióticos, es un fenómeno mundial y no hay ningún centro hospitalario que escape a esta realidad. Este incremento es multifactorial y se debe a la presión ejercida sobre las bacterias tanto en el medio ambiente hospitalario como en el extrahospitalario (8 ).
De todos es conocido el hecho de que los seres humanos abusamos de los antibióticos de muchas formas. Una de ellas es el empleo de antibióticos sin una justificación clínica real, otra es el empleo de ellos en el engorde animal o en el tratamiento de infecciones en vegetales. Por otro lado, está el uso de antibióticos sin prescripción médica por parte de los pacientes y el sugerir el uso de un antibiótico, por parte de los empleados de las farmacia (8 ).
Al Hospital Nacional de Niños, como centro de referencia pediátrico, llegan muchos pacientes con infecciones graves y algunos provienen de otros centros hospitalarios, se reciben pre medicados, lo que obliga al uso de antibióticos sin que medie un cultivo y menos una prueba de sensibilidad.
]]>Son tres los principales mecanismos utilizados por las bacterias para crear resistencia a los antibióticos:
Uno se presenta cuando las bacterias cambian sus proteínas fijadoras de penicilina (PBP,s) haciéndose inaccesibles a los antibióticos que necesiten de estas PBP,s para hacer su trabajo.
Otro se desarrolla con los cambios sufridos por la membrana externa de las bacterias Gram negativo, que la hacen impermeable a algunos antibióticos y que esto unido a la presencia de una bomba de eflujo que saca el antibiótico desde el espacio periplásmico al medio ambiente, produce entonces, el desarrollo de un tipo de resistencia muy especializado (8 ).
Finalmente, uno de los mecanismos más extendidos entre las bacterias es la producción de enzimas antidroga. En este último mecanismo podemos distinguir dos grandes formas. En una de ellas, hay producción de una enzima dirigida en forma específica hacia un antibiótico determinado, como es el caso de la cloranfenicol-acetil-transferasa, la cual es una enzima capaz de destruir la molécula del cloranfenicol (8 ). La otra forma es la producción de una beta lactamasa, una enzima que puede destruir el anillo beta lactámico de los antibióticos tipo penicilinas, cefalosporinas y sus derivados (8 ).
Además, las beta lactamasas son producidas tanto por bacterias Gram negativo como por Gram positivo, así como por bacterias aeróbicas. facultativas y anaeróbicas ( 8 ).
Hoy en día, se ha caracterizado una gran cantidad de estas enzimas y la clasificación de Bush, permite su estudio de una manera muy adecuada (1 ,6 ).
Dentro de las beta lactamasas, hay un tipo en el cual se produce una enzima inducible, que le confiere a la bacteria una resistencia de bajo nivel y que puede pasar desapercibida en el laboratorio, pero que se manifiesta en el paciente, en donde no hay actividad de la droga y por lo tanto, se presenta un fallo terapéutico (9 ).
Este tipo de beta lactamasas se conocen como las beta lactamasas de efecto expandido o ESBL por sus siglas en el idioma inglés (9 ).
Las cepas bacterianas capaces de producir ESBL, pueden ser clasificadas como multirresistentes, por lo que se aconseja que un bacilo Gram negativo de tipo entérico con multirresistencia debería ser estudiado como un posible productor de ESBL ( 8 ).
Estas cepas pueden ser estudiadas usando métodos manuales o métodos automatizados. En el caso de los métodos manuales, está la técnica de discos usando inhibidores de beta lactamasa y el E test. Dentro de los métodos automatizados está el uso de las tarjetas GNS-120 en el sistema automatizado Vitek ambos de la casa bioMerieux.
Material y Métodos
La División de Microbiología del Hospital Nacional de Niños cuenta con un sistema automatizado Vitek de la casa bioMerieux y se cuenta con las tarjetas GNS-120 capaces de detectar cepas bacterianas productoras de ESBL, así como con las tarjetas GNI+, empleadas en la identificación bioquímica de las cepas bacterianas. Este tipo de tarjeta se basa en la determinación de un bionúmero formado por 10 números, el cual, a su vez, puede ser utilizado como guía para evaluar la posibilidad de que las cepas sean bioquímicamente semejantes.
Durante un periodo de 12 meses, desde el l de enero al 31 de diciembre del 2002, se estudiaron 127 cepas de bacilos Gram negativo entéricos por la producción de ESBL. Las cepas se procesaron siguiendo el protocolo diseñado por la casa bioMerieux para estos fines y se emplearon, en todo momento, cepas frescas y crecidas en medios de cultivo no inhibitorios, Las cepas a estudiar provenían de niños internados o de consulta externa, atendidos en el Hospital Nacional de Niños durante el periodo de estudio.
Resultados
El porcentaje de positividad para Klebsiella pneumoniae fue de 77,9% (53 cepas), 100% para Klebsiella oxytoca (2 cepas) y 26,7% (4 cepas) para Escherichia coli.
De las 59 cepas aisladas, ESBL positivo, 53 correspondían a Klebsiella pneumoniae, 4 a Escherichia coli y 2 a Klebsiella oxytoca.
De las 59 cepas, dos correspondieron a dos paciente diferentes, que presentaron aislamientos de Klebsiella pneumoniae con diferentes bionúmeros, por lo cual se tomaron como cepas individuales. Se presentaron 10 aislamientos positivos por K. pneumoniae en heces, los que correspondían a niños con cultivos positivos en otras zonas del cuerpo y que el aislamientos de este agente en heces, se empleó como un indicador de colonización, lo que permitió un mejor manejo clínico del paciente.
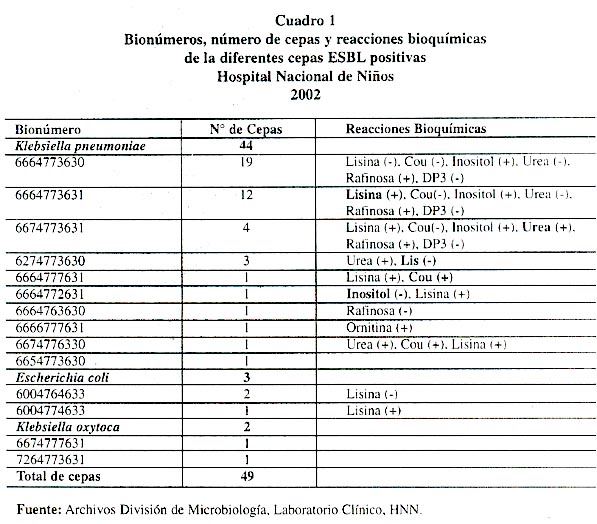
De las 59 cepas ESBL positivas, se pudo localizar el bionúmero en 49 de ellas, 44 para K. pneumoniae, 3 para E. coli y 2 para K. oxytoca, el bionúmero de identificación para K. pneumoniae 6664773630, fue el más frecuente, al encontrársele en 19 aislamientos, razón por la que lo empleamos como patrón. En el Cuadro 1 , se pueden observar los otros bionúmeros encontrados y sus desviaciones bioquímicas con respecto al patrón (bionúmero 6664773630).
Allí mismo podemos ver la similitud bioquímica existente entre las cepas de Klebsiella pneumoniae ESBL positivo aisladas en nuestro estudio.

En el Cuadro 2 se observa de qué tipo de muestra se aisló cada cepa ESBL positiva, siendo la muestra de sangre, seguida por la de heces, las más frecuentes.
]]> Es necesario hacer mención de que las puntas de catéter, el catéter venoso central y la sangre obtenida a través del catéter, si se unieran harían una cantidad de aislamientos que las pondría en el tercer lugar, con la acotación de que las infecciones asociadas a la colocación de un catéter revisten de una importancia adicional.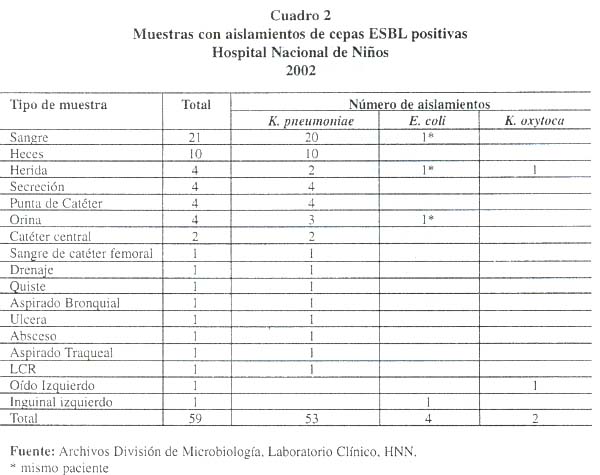
A su vez, en el Cuadro 3 , se muestran los aislamientos según servicio hospitalario, donde se evidencia que el servicio de Neonatología, aporta el mayor número de aislamientos, seguido por la Unidad de Cuidados Intensivos, lugares en donde se concentra la mayor cantidad de pacientes con antibióticoterapia prolongada.
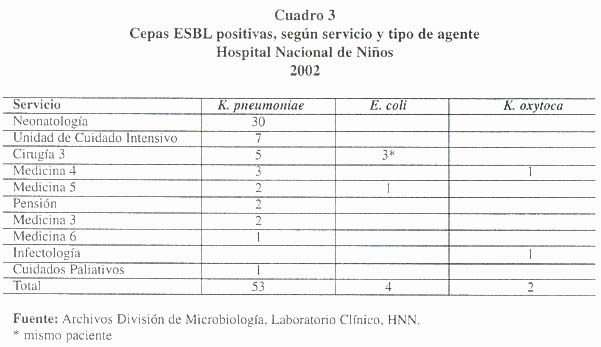
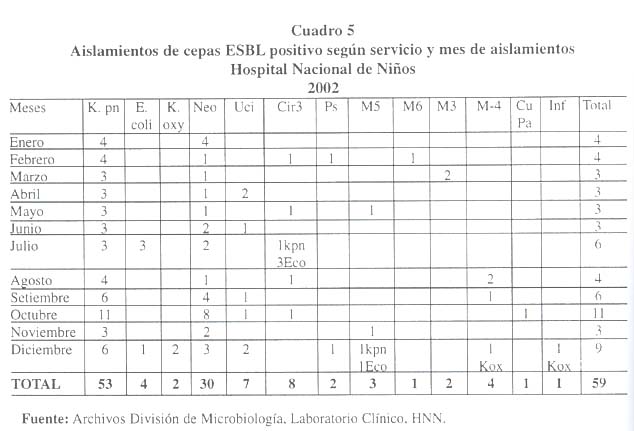
Por último en el Cuadro 5 , se presenta la información recabada según aislamiento de cepas ESBL positivas, con respecto a servicio hospitalario, mes de aislamiento y agente, donde vemos que los meses de octubre y diciembre presentan el mayor número de aislamientos de cepas ESBL positivo y que en especial en neonatología y durante el mes de octubre se presentó un brote con ocho aislamientos en el mes.
La definición de una beta lactamasa es clara, se trata de una enzima que tiene la capacidad de destruir el anillo beta lactámico, propio de los antibióticos que lo portan, como son las penicilinas y las cefalosporinas (1 ,2 , 8 ).
Se habla de esta enzima como no esencial, ya que su detección se produjo luego de la introducción al mercado de los antibióticos antes mencionados (8 ).
]]> Es una enzima que puede ser producida tanto por bacterias Gram positivo como por bacterias Gram negativo, con la única diferencia de que los Gram positivo la excretan al medio externo y los Gram negativo la vierten en su espacio periplásmico ( 9 ).Las beta lactamasas, comprenden una familia de proteínas de una enorme diversidad. por lo que se ha intentado su clasificación desde diversos puntos de vista. La clasificación de Bush. es la actualmente reconocida como la más adecuada y es una clasificación basada en la estructura molecular de la enzima, el sustrato sobre el que actúa y el posible inhibidor de su acción ( 1 ).
En el presente informe, se estudiaron una serie de bacterias aisladas a partir de muestras clínicas de pacientes pediátricos, en las cuales se detecta la producción de una beta lactamasa un poco diferente a las demás y que se conoce como beta lactamasa de efecto expandido o ESBL, por sus siglas en inglés.
La detección inicial de una ESBL se produjo en cepas de Klebsiella pneumoniae para luego ser encontrada en otras especies de la familia Enterobacteriaceae como la Escherichia coli (3 ,4 ,5 ). Es una enzima mediada por un plásmido y se deriva de una mutación sufrida por otras beta lactamasas tradicionales como la TEM 1 Y la SHV ( 8 ,9 ). Las ESBL, presentan susceptibilidad a los inhibidores de beta lactamasas como el clavulanato, el tazobactam y el sulbactam (8 ).
Las ESBL, se consideran enzimas inducibles, de difícil detección en el laboratorio y que se ponen de manifiesto en el paciente. Son de difícil detección a nivel de laboratorio, porque se trata de enzimas con un bajo nivel de expresión, pero que al contacto con el antibiótico en el paciente. se induce la producción de la enzima y de allí la resistencia observada y el consiguiente fallo terapéutico (6 ,8 ,9 ).
Se les conoce como beta-lactamasas de efecto expandido por su amplio rango de acción y de ser capaces de inhibir una gran variedad de antibióticos tales como cefotaxime, ceftriaxonc, ceftazidime, ceftizoxime y aztreonam (9 ).
De este grupo de enzimas, se conocen varias categorías, cada una de ellas con diferente actividad antibiótica y su encuentro es más frecuente en bacterias Gram negativo ( 2 ,9 ).
Varios autores sostienen que las cepas productoras de ESBL, deben ser consideradas como resistentes a todas las cefalosporinas, penicilinas y monobactans, aún cuando haya susceptibilidad in vitro (8 ,9 ).
Otro aspecto importante es que los genes productores de las ESBL, se encuentran unidos a otros genes de resistencia, por lo que podemos observar multirresistencia y en especial se observa resistencia a los aminoglucósidos y al trimetoprim sulphamethozaxole ( 3 ).
Los métodos de detección para cepas productoras de ESBL, se pueden dividir en métodos manuales y métodos automatizados. Dentro de los métodos manuales, tenemos el uso de la técnica de doble disco, donde en un plato de agar Mueller-Hinton, rayado con la cepa en estudio. se colocan discos de un sustrato (cefotaxime) y a 20 ó 30 mm de largo un disco con un inhibidor de beta lactamasa (amoxicilina / ácido clavulánico) y luego del periodo de incubación se observa. en caso de ser positivo, un halo característico en forma de corcho de una botella de champagne. Otro método manual es el empleo de tiras de E-Test específicas para la detección de estas cepas (2 ,3 ,8 ,9 ) . Dentro de los métodos automatizados se encuentra el uso de la tarjetas GNS-120 del sistema Vitek de la casa comercial bioMerieux.
En cuanto a los resultados observados en nuestra serie, encontramos casi un 50% de positividad en las cepas analizadas, donde destaca Klebsiella pneumoniae como la más frecuente, seguida por Escherichia coli, lo cual concuerda con lo observado en la literatura (3 ,4 ,5 ,7 ).
De las 44 cepas de Klebsiella pneumoniae encontradas como productoras de ESBL, vemos como la mayoría de ellas son aisladas en pacientes que provienen del servicio de Neonatología, donde la sangre, las heridas y las puntas de catéter constituyen la gran mayoría de las fuentes.
Utilizando los bionúmeros obtenidos en la identificación de las especies en el sistema Vitek, podemos concluir que hay una muy buena similitud entre estos aislamientos. Como se observa en el Cuadro 1 , de 44 cepas de Klebsiella pneumoniae, 19 tienen el mismo bionúmero y las restantes presentan variaciones muy sutiles en la actividad sobre determinados sus tratos. Así por ejemplo, si la cepa con el bionúmero 6664773630 no utiliza la lisina como sus trato, la cepa con el bionúmero 6664773631 sí la utiliza.
No hay duda de que se requieren estudios moleculares para definir que se trata de la misma cepa, pero en vista de estos datos, de que provienen de pacientes semejantes y de muestras semejantes podríamos decir, con bastante certeza, que se trata de la misma cepa.
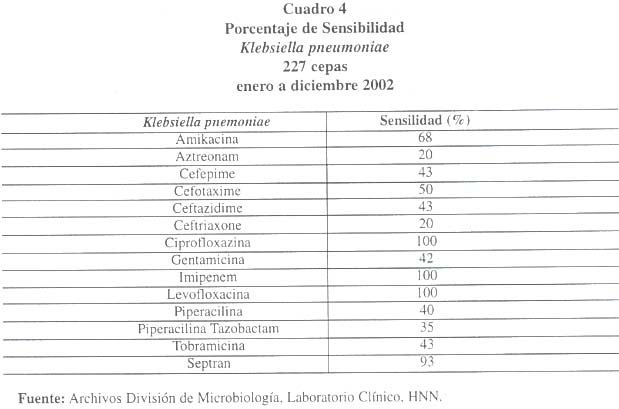
Para concluir, tenemos serios problemas de resistencia hacia los antibióticos en las cepas de Klebsiella pneumoniae aislados en el Hospital Nacional de Niños, con altos niveles de resistencia a las cefalosporinas de tercera generación y a los aminoglucósidos y que esto puede ser atribuido al hecho de que gran parte de estas cepas son productoras de beta lactamasas de efecto ampliado, por lo que se sugiere tener un mejor control del uso de los antibióticos así como mejorar la detección de patrones de resistencia intrahospitalaria.
Resumen
]]>Entre las bacterias, la resistencia antimicrobiana ha crecido en forma alarmante en los últimos años y en este campo se ha avanzado mucho, en especial, en los métodos de detección de esta resistencia, dentro de los cuales se destaca la beta lactamasa de efecto expandido o ESBL para la cual se empleó un método automatizado. Se estudiaron 127 cepas para un 46.5% de positividad general, siendo Klebsiella pneumoniae la bacteria más frecuente con un 77.9% de presentación, seguida por Escherichia coli y Klebsiella oxytoca. Se demuestra que en las unidades de Neonatología y Cuidados Intensivos se aislan cepas ESBL positivo con mayor frecuencia.
Bibliografía
1. Bush K., Jacoby G.& Madeiros A: A functional cIassifications scheme for _-Iactamases and its correlation with molecular structure. Antimicob. Agents Chemother. 39: 1211, 1995. [ Links ]
2. Jacoby O. & Madeiros A: More extended-spectrum _-Iactamases. Antimicrob. Agents Chemother. 35: 1697, 1991. [ Links ]
3. Jacoby O. & Han P.: Detection of extended-spectrum _-Iactamases in cIinical isolated of Klebsiella pneumoniae and Escherichia coli. J. Clin. Microbiol. 34: 908. 1996. [ Links ]
4. Jarlier V., Nicolas M., Fournier O. & Philippon A: Extended broad-spectrum _-Iactamases conferring transferable resistance to newer _-Iactam agents in Enterobacteriaceae: hospital prevalence and susceptibility patterns Rev. Inf. Dis. 10: 867, 1988. [ Links ]
5. Katsanis G., Spargo J., Ferraro M. et al.: Detection of Klebsiella pneumoniae and Escherichia coli strains producing extended -spectrum beta-Iactamases J. Clin. Microbiol. 32: 691, 1994. [ Links ]
6. Livermore D.: _-Lactamases in laboratory and clinical resistance Clin. Microbiol. Rew. 8: 557, 1995. [ Links ]
7. Livermore D. & Yuam M.: Antibiotic resistance and production of extended-spectrum -lactamases amongst Klebsiella spp. from intensive care units J. Antimicrob. Chemother. 3 8 : 409. 1996. [ Links ]
8. Quintiliani R., Sahm D.& Courvalin P.: Mechanism of Resistance to Antimicrobial Agents In: Manual of Clinical Microbiology 7th ed. Editors in chief Patrick Murray. Eds Baron E.. et al. America Society of Microbiology Washington DC. 1999.
9. Swenson J., Hindler J. & Peterson L.: Special Phenotypic Methods for Detecting Antibacterial Resistance In: Manual of Clinical Microbiology 7th ed. Editors in chief Patrick Murray. Eds Baron E., et al. American Society of Microbiology Washington DC. 1999. [ Links ]
* División de Microbiología, Laboratorio Clínico, Hospital Nacional de Niños. Caja Costarricense de Seguro Social. San José, Costa Rica. mherrera@hnn.sa.cr