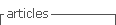Services on Demand
Journal
Article
Indicators
-
 Cited by SciELO
Cited by SciELO -
 Access statistics
Access statistics
Related links
-
 Similars in
SciELO
Similars in
SciELO  uBio
uBio
Share
Revista de Biología Tropical
On-line version ISSN 0034-7744Print version ISSN 0034-7744
Rev. biol. trop vol.59 n.2 San José Jun. 2011
Filogenia de hongos roya (Uredinales) en la zona andina colombiana mediante el uso de secuencias del ADN ribosomal 28S
Catalina Zuluaga1, Pablo Buriticá2 & Mauricio Marín1
1.Universidad Nacional de Colombia sede Medellín, Laboratorio de Biología Celular y Molecular, Cra 64 x Calle 65, Autopista Norte, Medellín, Colombia; catazuluaga81@gmail.com, mamarinm@unal.edu.co
2.Universidad Nacional de Colombia sede Medellín, Departamento de Ciencias Agronómicas, Cra 64 x Calle 65, Autopista Norte, Medellín, Colombia; pburitica@unal.edu.co
Dirección para correspondencia
Abstract
Phylogenetic analysis of rust fungi (Uredinales) from the Colombian Andean region using 28S ribosomal DNA sequences. Rust fungi (Uredinales, Basidiomycetes) are one of the most diverse and economically important plant-obligated parasites. Taxonomy of this group has been under revision during the last years using molecular techniques to define phylogenetic relationships. In this study we evaluated the phylogenetic affinities of a group of 40 rust fungi obtained from different plants in the Colombian Andean region using sequence analysis of the 28S ribosomal DNA, specifically D1/D2 domains. Comparisons were undertaken with sequences of rust fungi from around the world deposited in the GenBank database. An alignment of sequences was used to build a phylogenetic tree through Maximum parsimony analysis. Our results support the taxo- nomical validity of families Pucciniaceae, Phakopsoraceae, Phragmidiaceae, Pileolariaceae, Mikronegeriaceae, Coleosporiaceae and Cronartiaceae, while Pucciniosiraceae represents redundant taxa with Pucciniaceae. The analyses indicated that Uropyxidaceae, Raveneliaceae, Chaconiaceae and Pucciniastraceae correspond to poly- phyletic families. Melampsoraceae appear to be a basal taxon to the Uredinales. information obtained in this study will be useful to incorporate a higher number of sequences from tropical rust fungi within global efforts to redefine the taxonomy of order Uredinales. Additionally, we propose to give priority to future phylogenetic studies of taxa: Gerwasia, Hemileia, Phragmidium, Prospodium, Puccinia and Uromyces, genera that include a high number of rust fungi from the tropics. Rev. Biol. Trop. 59 (2): 517-540. Epub 2011 June 01.
Key words: maximum parsimony, rDNA, rust fungi, sequence analyses.
Resumen
Los hongos roya (Uredinales, Basidiomycetes) representan uno de los grupos de fitoparásitos más diversos y con mayor importancia económica agrícola mundial. Su taxonomía se ha basado en el estudio de caracteres morfológicos, que resulta en muchos casos en la formación de taxones polifiléticos. Sin embargo, en los últimos años se han tratado de incorporar herramientas moleculares que conduzcan a la generación de sistemas de clasificación basados en afinidades evolutivas. Este trabajo pretendió aumentar la base del conocimiento sobre la uredobiota tropical, mediante el estudio de características morfológicas y filogenéticas de un grupo de royas de los Andes de Colombia. Para esto se secuenció parte de la región 28S del ADNr y se realizó un análisis de agrupamiento mediante Máxima parsimonia. Los resultados confirmaron la validez de las familias Pucciniaceae, Phakopsoraceae, Phragmidiaceae, Pileolariaceae, Mikronegeriaceae, Coleosporiaceae y Cronartiaceae, mientras que Pucciniosiraceae es un taxón redundante con Pucciniaceae. Por su parte, Uropyxidaceae, Raveneliaceae, Chaconiaceae y Pucciniastraceae se muestran como familias polifiléticas. Aparentemente Melampsoraceae se presenta como un taxón basal al grupo. La información que se deriva de este estudio se espera sea incorporada en los estudios mundiales que buscan redefinir el sistema taxonómico de los hongos roya.
Palabras clave: ADNr, hongos roya, máxima parsimonia, puccinia, secuenciación.
Los hongos roya (Urediniomycetes, Uredinales) constituyen uno de los grupos de hongos más numeroso, diverso y de amplia distribución mundial (Buriticá 2003a); son parásitos obligados (holobiótrofos) de un amplio rango de plantas incluidas helechos, coníferas y angiospermas, con las cuales han coevolucionado, que adaptan su ciclo de vida a las condiciones ecológicas del hábitat de sus hospedantes (Buriticá 2001, Buriticá 2003b, Cummins & Hiratsuka 2003, Zuluaga et al. 2009). Los Uredinales son conocidos como royas por la inducción de pústulas que contienen esporas con apariencia de un polvillo herrumbroso sobre los tejidos de sus hospedantes; sin embargo, también pueden causar hipertrofias e hiperplasias, escobas de bruja y formación de pseudoflores (Cummins & Hiratsuka 2003).
El orden Uredinales está conformado por 13 familias, 163 géneros y unas 7 000 especies (Hawksworth et al. 2001); aunque se estima que el grupo puede contener de 20 000 a 24 000 especies (Buriticá 2003b). Recientemente, Bauer et al. (2006) en su estudio de los Basidiomycetes con septos simples, sugirieron renombrar las categorías suprafamiliares en que se ubican los hongos roya como orden Pucciniales de la clase Pucciniomycetes. Los hongos roya pueden producir hasta cinco estados espóricos que se designan como: espermogonio (espermacios e hifas receptivas) (O), aeciospora (I), uredospora (II), teliospora (III) y basidiospora (IV) (Hahn 2000). Cada estado espórico es morfológica y funcionalmente diferente dentro del ciclo de vida de las especies de royas (Hawksworth et al. 2001, Cummins & Hiratsuka 2003).
La clasificación de los Uredinales a nivel genérico y supragenérico ha sido basada casi exclusivamente en la morfología de los telio-soros y teliosporas. Inicialmente dos familias fueron definidas por las características morfológicas de sus teliosporas: Melampsoraceae con teliosporas no pediceladas (teliosoros subepidermales, cubiertos) y Pucciniaceae con teliosporas pediceladas (teliosoros erumpentes) (Dietel 1928). Posteriormente, Gaumann (1949) adicionó las familias Pucciniastraceae (teliosoros inmersos), Cronartiaceae (teliosoros columnares), Chrysomyxaceae (teliosoros cupulares) y Coleosporiaceae (basidio interno). Cummins & Hiratsuka (1983) propusieron la definición de 14 familias para el orden Uredinales, las cuales luego redujeron a 13, una vez unidas las familias Raveneliaceae y Sphaerophragmiaceae (Cummins & Hiratsuka 2003).
La taxonomía de hongos se ha fundamentado tradicionalmente en el empleo de caracteres morfológicos. En muchos casos estas características son variables, que producen información insuficiente o poco precisa que conduce a la generación de clasificaciones no naturales. En las últimas décadas, la secuenciación de regiones ribosomales y funcionales ha jugado un papel fundamental en la inferencia de las relaciones evolutivas entre individuos y grupos de individuos (Sugiyama 1998, Blackwell et al. 2006). Sin embargo, el número de estudios que emplean estas herramientas moleculares para la realización de estudios taxonómicos en hongos roya es muy reducido, en comparación con aquellos realizados en otros grupos de hongos (Zuluaga et al. 2009), siendo son los más destacados aquellos realizados por Maier et al. (2003, 2007), basados en la secuenciación de una porción de la región 28S del ADNr en hongos roya recolectados principalmente en Europa y que pusieron de manifiesto que los géneros Puccinia, Pucciniastrum, Thekopsora y Uromyces son polifiléticos, mientras que Chrysomyxa, Coleosporium, Cronartium, Gymnosporangium, Melampsora, Phragmidium y Tranzschelia, representan taxones monofiléticos. La condición polifilética de los géneros Puccinia y Uromyces fue confirmada posteriormente por van der Merwe et al. (2007) quienes usaron análisis de secuencias de los genes del factor de elongación 1α y β-tubulina 1. Un estudio similar fue realizado por Wingfield et al. (2004), pero mediante análisis de secuencias de la subunidad pequeña del ADNr en 64 especies de 12 familias de royas; en este caso se encontró que los géneros que presentan estados aeciales sobre gimnospermas están filogenéticamente distantes de los hongos roya que desarrollan dicho estado sobre plantas angiospermas; además se determinó que la condición de autoicismo/heteroicismo no representa un carácter taxonómico válido y que familias como Pucciniaceae y Pucciniastraceae representan taxones polifiléticos.
Aime (2006) utiliza la estrategia de combinar datos de ambas subunidades ribosomales, al realizar un estudio tendiente a evaluar el soporte filogenético de las familias del orden Uredinales propuestas por Cummins & Hiratsuka (2003) con base en caracteres morfológicos. De las trece familias propuestas, ocho (Coleosporiaceae, Melampsoraceae, Mikronegeriaceae, Phakopsoraceae, Phragmidiaceaeae, Pileolariaceae, Pucciniaceae y Raveneliaceae) están bien soportadas por el análisis basado en secuencias, mientras que tres son redundantes (Cronartiaceae, Pucciniastraceae y Pucciniosi-raceae), y en dos de ellas, su condición no pudo ser definida (Chaconiaceae y Uropyxidaceae).
A pesar del alto número de especies de royas presentes en los trópicos, el nivel de conocimiento que se tiene de estos hongos en esta región es incipiente, tanto desde el punto de vista biológico como en lo relacionado a su clasificación taxonómica. Esta situación contrasta con la gran importancia económica que presentan algunas royas en diversos agroecosistemas tropicales y con el potencial bioprospectivo de especies que podrían ser utilizadas como biorreguladores de plantas arvenses. Una de las regiones neotropicales de las que se posee menor conocimiento sobre este grupo de organismos, es la zona andina que comprende una franja altitudinal entre 2 000 y 4 600m.s.n.m, nicho ecológico que ofrece condiciones físicas y biológicas muy particulares, y específicamente para el caso de hongos roya incluye fundamentalmente especies con ciclos de vida reducido, poco abordadas en los estudios micológicos mundiales que utilizan herramientas moleculares (Zuluaga et al. 2009), aunque parcialmente evaluadas en estudios morfológicos (Buriticá 1991, Buriticá 1994, Buriticá 2000, Pardo-Cardona 2001, Salazar 2002, Buriticá 2003a).
En esta investigación se llevo a cabo una recolección de hongos roya procedentes de plantas cultivables y silvestres de diversas regiones de la zona andina de Colombia, para el estudio de sus características morfológicas y relaciones filogenéticas, como una estrategia para aumentar el nivel de conocimiento que se posee de este grupo de hongos en el trópico, así como para evaluar las hipótesis taxonómicas recientemente apoyadas en estudios moleculares sobre el carácter filogenético de las diferentes familias tradicionalmente propuestas dentro del orden Uredinales.
Materiales y métodos
Recolección de muestras: Las muestras fueron recolectadas en diferentes regiones de cinco departamentos de la zona andina de Colombia (Antioquia, Boyacá, Cundinamarca, Risaralda y Tolima) (Fig. 1), incluye el sistema de páramos y bosques altoandinos del noroccidente medio antioqueño (Belmira, Yarumal), además de las zonas andinas del suroccidente antioqueño (Caramanta, Tamésis, valparaíso). También se incluyeron muestras de regiones montañosas de los departamentos de Boyacá (Sogamoso, Sora), Cundinamarca (Bojacá, El Rosal, Pacho, Subachoque, Tausa, Villa Pinzón, Zipaquirá) Caldas (Manizales, villa María), Risaralda (Quinchia) y Tolima (Páramo de Letras) (Cuadro 1). Para la obtención de las muestras se realizó un recorrido por vías primarias y secundarias de cada uno los sitios descritos, se evaluó la presencia de plantas con síntomas y signos de royas, ante lo cual se tomaban los órganos y tejidos afectados (generalmente al menos una hoja). De esta forma, cada muestra estaba representada por diferentes pústulas de royas en tejidos de una misma planta y dependiendo de la uredobiota presente en cada sitio de muestreo, el número de especímenes recolectados variaba entre zonas. Cada muestra recolectada fue prensada para evitar su deterioro junto con su respectiva información referente al hospedante y a las características geográficas de la zona. Las muestras fueron llevadas al Herbario MEDEL de la Universidad Nacional de Colombia sede Medellín, para su secado e identificación botánica y los especímenes así procesados fueron depositados en el Museo Micológico de la Universidad Nacional de Colombia Sede Medellín (MMUNM).
Caracterización morfológica: La descripción morfológica de los especímenes recolectados incluyó las siguientes observaciones de las pústulas: posición respecto al tejido del hospedante, color, forma, agrupación y consistencia. De cada estado espórico encontrado se realizaron micropreparados para describir su forma, color, ornamentación, número y posición de poros; dimensiones; tamaño de la pared apical y lateral; presencia, posición, ornamentación y largo de pedicelos; presencia de estructuras estériles como parafisos y peridio. Cada muestra fue comparada con especímenes de referencia ubicados en la colección del MMUNM y la Colección Nacional de Royas de Colombia de la Facultad de Ciencias Agropecuarias. Además se utilizaron las monografías taxonómicas de hongos Uredinales (Cummins 1940, 1971, 1978, Buriticá & Hennen 1980, Hennen et al. 1982, Cummins & Hiratsuka 1991, Buriticá 1991, 1994, 1999 a,b, Pardo-Cardona 1999, Salazar 2002, Hennen et al. 2005, Salazar et al. 2007) y las bases de datos del Index Fungorum (CABI et al. 2008) y del catálogo de especies tipo de hongos roya del Jardín Botánico de New York (The New York Botanical Garden Herbarium 2003).
Extracción de ADN: De cada una de las royas se realizó la extracción de ácidos nucleicos mediante dos metodologías: método convencional CTAB 2X/Fenol/Cloroformo y Kit comercial DNAeasy Plant Mini (Qiagen, CA, EEUU), cuyo procedimiento se basó en las instrucciones del fabricante. En ambos casos se partió de uno o varios soros, que dependen de su tamaño y grado de esporulación, y se toma la menor cantidad de tejido vegetal posible para su ubicación en un tubo eppendorf de 1.8mL. En el método convencional los tubos se colocaron en un recipiente con nitrógeno líquido para proceder a la maceración del tejido en presencia de 200µL del buffer CTAB 2X (CTAB 2%, NaCl 1.4M, EDTA 20mM, Tris-HCl 100mM pH 8.0) y 1% de β-Mercaptoetanol, incubándose a 65°C durante 10min. Luego se separó la fase orgánica mediante 1vol. de fenol:cloroformo (1:1) y se centrifugó a 13 000 rpm por 10min. De acuerdo al grado de pureza del sobrenadante, este procedimiento se repitió, pero con el uso de un sólo vol de cloroformo. Para precipitar los ácidos nucleicos se emplearon 2vol de etanol absoluto y 0.1vol de acetato de sodio 3M, y se colocaron los tubos a -20ºC durante al menos 30min, tiempo después del cual se centrifugó a 13 000 rpm por 15min. El microprecipitado resultante se lavó con etanol al 70% y finalmente se resuspendió en 20µL de agua destilada estéril, para su utilización en las amplificaciones de PCR. La cantidad de ADN obtenida se determinó por espectrofotometría a 260nm de longitud para lo cual se utiliza un espectro Thermo Scientific, Genesys 6 (Waltham, MA, EEUU).
Amplificación y secuenciación del ADNr 28S: Para la PCR se emplearon los cebadores LROR (5’ ACC CGC TGA ACT TAA GC 3’) y LR6 (5’ CGC CAG TTC TGC TTA CC 3’) que amplifican una región del extremo 5’ de la subunidad grande del ADNr que contiene los dominios D1 y D2, ampliamente utilizados para estudios filogenéticos de hongos (Guadet et al. 1989, Hopple & Vilgalys 1999). La amplificación de PCR se realizó en un termociclador T3 (Biometra, Göttingen, Alemania) y consistió de una modificación del programa propuesto por Vogler & Bruns (1998), con una desnaturalización inicial a 94°C por 3min, seguido por 35 ciclos de 94°C por 1.30min, 50°C por 1min, 72ºC por 1min y una extensión final a 72°C por 7min. Las reacciones se realizaron en un volumen total de 25 µL, que contiene 0.5µM de cada cebador, 1U de Taq ADN polimerasa recombinante (Fermentas, Vilnius, Lithuania), 0.2mM de cada dNTP, 1X de buffer de enzima (100mM Tris-HCl pH 8.8, 500mM KCl, 0.8% Nonidet P40), 1.8mM MgCl 2, 1µL de ADN [100 - 1000ng/µL] y agua destilada ésteril. Luego de la amplificación se tomaron 5µL de los productos de reacción para analizarlos por electroforesis en gel de agarosa al 1.5% suplementado con 0.5 µg/mL de bromuro de etidio en buffer de corrido TBE 0.5X (45mM Tris-Borato, 1mM EDTA pH 8.0). La visualización de las bandas amplificadas se realizó bajo luz ultravioleta en un transiluminador automático Bio Doc Analyze (Biometra). Una vez definida la especificidad y tamaño de los productos amplificados, se procedió a su purificación utilizando los kits Wizard PCR Preps ADN Purification System (Promega, Madison, EEUU) y QiAquick PCR Purification Kit (Qiagen, CA, USA) para proceder a su secuenciación directa mediante el sistema Big Dye Terminator Cycle Sequencing Ready Reaction (PE Applied Biosystems, Foster City, EEUU) y su corrido en un secuenciador ABI Prism 3730xl (PE Applied Biosystems) de la compañía Macrogen (Corea del Sur).
Resultados
Colección de muestras: En total se identificaron 100 especímenes de hongos roya con base en sus caracteres morfológicos a partir de 238 muestras de hospedantes (Cuadro 1). Del total de muestras identificadas, 25 fueron obtenidas de plantas de la familia Asteraceae y 14 de la familia Solanaceae. Una sola roya fue obtenida de plantas de las familias Alstroemeriaceae, Apiaceae, Apocynaceae, Bromeliaceae,Cannaceae, Cucurbitaceae, Denstaedtiaceae, Liliaceae, Malvaceae, Moraceae y Piperaceae; dos de Betulaceae, Lamiaceae, Malpighiaceaey Oxalidaceae; tres de Convolvulaceae y ver-benaceae; cuatro pertenecieron a Euphorbiaceae y Polygonaceae; seis a Rubiaceae, siete a Rosaceae y nueve a Fabaceae y Poaceae. No fue posible identificar botánicamente una muestra por falta de material (Cuadro 1).
Caracterización morfológica: Las 100 muestras identificadas correspondieron a 61 especies diferentes con la siguiente distribución: dos especies de las familias Pucciniastraceae, Coleosporiaceae, Mikronegeriaceae,Uropixydaceae, Phragmidiaceae; tres especies de Chaconiaceae; cuatro especies de Pucci-niosiraceae y Phakopsoracea; 33 especies de Pucciniaceae y siete muestras correspondieron a estados anamórficos identificados como Uredo sp. y Aecidium sp. En el Cuadro 3 se presentan los resultados de las mediciones de los estados espóricos encontrados en un representante de las 61 especies identificadas. Las dimensiones corresponden al formato: medición mínima - medición máxima (promedio;desviación éstandar). Las descripciones para cada especie se encuentran disponibles en el material anexo asociado a este manuscrito.
Amplificación y secuenciación de ADNr28S: Con la metodología de extracción de ADN convencional se obtuvieron 68 amplicones. En aquellas muestras en las que luego de varios intentos de amplificación por PCR no fue posible obtener el fragmento esperado, se procedió a la extracción de ADN mediante el kit comercial de Qiagen, se obtuvieron 32 amplicones adicionales. La secuenciación del fragmento amplificado se realizó en ambas direcciones en reacciones individuales con cada uno de los cebadores utilizados en el PCR. Luego de varios intentos, se obtuvieron ambas secuencias en 40 de las royas recolectadas, no se incluyeron en el análisis posterior las royas para las que se generaron secuencias en un sólo sentido, pues esto implicaba reducir el número de sitios para el análisis de MP. Una vez editadas las secuencias y construidos los consensos, se determinó que el tamaño de este fragmento oscilaba entre 1 080 y 1 170 pb, según la especie de roya. Pero, con el fin de homogenizar los extremos de las secuencias, fue necesaria su edición, obteniéndose entre 1 000 y 1 100 pb. Las secuencias fueron depositadas en el GenBank y sus números de accesión se registran en el Cuadro 3.
Análisis filogenético: Para el análisis filogenético se incluyeron secuencias de 89 especímenes, 49 obtenidas del Genbank y las 40 generadas en esta investigación. El alineamiento final de las secuencias alcanzó 1 176 sitios, de los cuales 434 caracteres eran constantes, 236 variables pero no informativos y 506 informativos. La longitud del árbol filogenético con máxima parsimonia fue de 4 585, con índices de consistencia (IC) y retención (IR) de 0.315 y 0.53, respectivamente (Fig. 2). En el dendrograma se presentaron siete clados bien definidos, algunos de los cuales contienen subgrupos internos, así como ramas individuales (Fig. 2).
El clado I albergó un alto número de especímenes (29) recolectados en esta investigación, así como secuencias obtenidas del GenBank que representan especies de los géneros Puccinia, Uromyces, Cumminsiella y Miyagia, razón por la cual se infiere que este grupo corresponde a la familia Pucciniaceae. Adicionalmente, el clado incluyó la secuencia de referencia de Aecidium kalanchoe, lo que puede implicar que este taxón represente el estado anamórfico de una especie de la familia Pucciniaceae. Un aspecto relevante del análisis, es el hecho que aquellos especímenes identificados morfológicamente como pertenecientes a los géneros Chardoniella y Pucciniosira, adscritos a la familia Pucciniosiraceae, fueron incluidos en este clado, al igual que las secuencias de referencia de las especies Pucciniosira pallidula y Dietelia portoricensis. El clado I presentó dos subgrupos medianamente soportados por el análisis de bootstrap. El subgrupo IA, incluye cuatro clados bien soportados estadísticamente: IA-1: corresponde a varios especímenes identificados en este estudio como Chardoniella gynoxidis y Chardoniella sp.; IA-2: conformado por las especies identificadas como Pucciniosira solani y Pucciniosira sp.; IA-3: incluyó la secuencia referencia de Puccinia coronata y las especies identificadas morfológicamente en este estudio como P. coronata y P. striiformis; IA-4: contiene las especies Puccinia peperomiae y una especie del género Maravalia (M. guianensis). Los demás integrantes del subgrupo IA se presentan en ramas individuales o clados con bajo soporte estadístico.
El subgrupo IB presenta dos clados bien soportados, IB-1: incluye las especies Puccinia spegazzinii, mientras que IB-2 contiene las especies P. vernoniae-mollis, P. eupato-rii-colombiani y Pucciniosira pallidula. Los demás integrantes del subgrupo IB corresponden a ramas individuales o clados con bajo soporte estadístico donde están incluidos P. cnici-oleracei, P. hydrocotyles, P. thaliae, U. novissimus (recolectados en este trabajo) y la secuencia de referencia de la especie Dietelia portoricensis, entre otras.
El clado II se ubica en posición basal con respecto al clado I e incluye diferentes secuencias referencia de especies representativas de la familia Pucciniaceae: Gymnosporangium juniperi-virginianae y Puccinia podophylli, además contiene las especies anamórficas Uredo chusqueae y U. baruensis. La secuencia obtenida del GenBank de Kweilingia divina, adscrita a la familia Phakopsoraceae está incluida en este grupo, con un fuerte soporte estadístico y presenta una gran afinidad con el espécimen U. chusqueae.
El clado III está conformado por secuencias de especies representativas de las familias Coleosporiaceae, Cronartiaceae y Pucciniastraceae. Los únicos especímenes del clado colectados en este estudio, fueron identificado morfológicamente como Coleosporium ipomoea, C. vernoniae y una especímen anamórfico determinado como Uredo sp. Caduna de las familias incluidas en este clado presenta un fuerte soporte estadístico en el análisis de bootstrap.
El clado IV representa la familia Phakop soraceae con secuencias de tres géneros Phakopsora, Arthuria y Batistopsora. Además el grupo incluye los especímenes colectados Phakopsora meibomiae y Arthuria sp. El análisis asocia este grupo con la especie Prospodium lippiae, que pertenece a la familia Uropyxidaceae.
El clado V representa los miembros de la familia Phragmidiaceae al incluir secuencias de los géneros Frommeella, Kuehneola, Trachys pora y Gymnoconia.
El clado VI está fuertemente soportado (100%) e incluye dos especies del género Endo raecium, perteneciente a la familia Pileolariacea.
El clado VII está conformado únicamente por dos especies del género Ravenelia (familia Raveneliaceae), además de los especímenes colectados Chrysocelis muehlenbeckiae Chrysocyclus cestri, que representan especie de las familias Mikronegeriaceae y Pucciniaceae, respectivamente.
Además de los clados mencionados, e árbol filogenético presenta una serie de especies dispersas a lo largo del dendrograma, entre las que se destacan el grupo formado por la especie recolectada Uredo zeugites y la secuencia de referencia de Puccinia physalidis; además de las especies Sphenospora kevorkian (Raveneliaceae), asociados al clado I; mientras que las especies Hemileia colombiana y H. vastatrix, no se presentan relacionadas. Finalmente, se destaca que la ubicación taxonómica de las especies Tranzschelia discolor (Uropyxidaceae), Olivea scitula (Chaconiaceae), Melampsoridium betulinum y Melampsora epgea, no es claramente definida por el anális de MP realizado.
Discusión
En este trabajo se realizó un estudio morfológico y filogenético basado en la secuenciación de la subunidad grande (28S) del ADNr de 40 hongos roya recolectados en la región andina de Colombia, estableciéndose sus afinidades con 47 especies (que incluyen especímenes tanto del trópico como de la zona templada), cuyas secuencias se encuentran disponibles en el GenBank y representan al menos un género de cada una de las trece familias propuestas por Cummins & Hiratsuka (2003). Esta investigación se realizó con el ánimo de incluir información referente a hongos roya neotropicales en los estudios recientes que tratan de dilucidar las relaciones evolutivas de los Uredinales y que buscan redefinir su sistema taxonómico.
La validez taxonómica del orden Uredinales (Pucciniales) dentro del Subphylum Puccininiomycotina, ha sido confirmada en dos estudio filogenéticos independientes que utilizaron las secuencias de las subunidades grande y pequeña del ADNr (Aime et al. 2006, Bauer et al. 2006), y que concluyeron que éste representa un grupo monofilético dentro de la Clase Pucciniomycetes; la cual comparte con los ordenes Platygoeales, Heliocobasidiales y Septobasidiales, grupos de los cuales fueronseleccionados los taxones externos empleadosen nuestro estudio filogenético (E. muscicolay S. taxodii) y cuya ubicación en el análisis realizado, ocurrió en forma externa al grupo de los Uredinales.
Tradicionalmente, la taxonomía de los Uredinales se ha basado en el empleo de caracteres morfológicos, cuya ponderación ha variado dependiendo de cada uno de los sistemas planteados. Esta situación ha conducido a propuestas que dividen el orden en dos familias (Dietel 1928) basadas en la estructura de las telioporas (Pucciniaceae: teliosoros erumpentes con teliosporas pediceladas y Melampso- raceae: teliosoros subepidermales, cubiertos y teliosporas sésiles), hasta clasificaciones más complejas que separan el grupo en 13 (Cummins & Hiratsuka 2003), 14 (Cummins & Hiratsuka 1983) ó 16 familias (Buriticá,1999a,b), de acuerdo con la estructura de las teliosporas, el tipo de espermogonio, y en algunos casos las características de los aeciosoros, uredosporas y basidios (Hiratsuka & Hiratsuka 1980). Estudios filogenéticos recientes basados en la secuenciación del ADNr y de algunos genes nucleares (Maier et al. 2003, Wingfield et al. 2004, Aime 2006, Bauer et al. 2006, van Der Merwe et al. 2007) revelan incongruencias a todos lo niveles taxonómicos con la clasificación basada en caracteres morfológicos. Así por ejemplo, Maier et al. (2003) indican que los géneros Puccinia, Pucciniastrum, Thekopsora y Uromyces son claramente polifiléticos, mientras que Aime (2006) encontró que las familias Cronartiaceae, Pucciniastraceae y Puc-ciniosiraceae se presentan como redundantes, mientras que Chaconiaceae y Uropyxidaceae corresponden a taxones no naturales.
En nuestro estudio resultó evidente la separación de Pucciniaceae sensu lato del linaje Melampsoraceae sensu lato (Coleosporaceae, Pucciniastraceae, Cronartiaceae). Sin embargo, el primer grupo se presentó disperso a lo largo del dendrograma, mientras que Melampsoraceae sensu lato sí correspondió a un solo clado (III), aunque Melampsora epigea, la única especie analizada de la familia Melampsoraceae sensu stricto, se ubicó por fuera de ambos grupos, en posición basal. Esta situación fue igualmente encontrada por Maier et al. (2003), quienes proponen que el género Melampsora representa un linaje primitivo del orden Uredinales, caracterizado por su falta de especificidad y la diversidad de relaciones que sus especies establecen con sus hospedantes (Durrieu 1980). Es claro que esta hipótesis sólo puede ser confirmada incluyendo en análisis posteriores un mayor número de especímenes pertecientes a este género y especialmente de hospedantes tropicales ancestrales, tales como los helechos.
El linaje Pucciniaceae sensu lato se caracteriza por presentar especies que cuando son heteroicas, desarrollan aecios sobre angiospermas. Este grupo ha sido subdividido por Cummins & Hiratsuka (2003) con base en el tipo de espermogonio en nueve familias: Mikronegeriaceae, Phakopsoraceae, Chaconiacecae, Uropyxidaceae, Pileolariaceae, Raveneliaceae, Phragmidiaceae, Pucciniaceae y Pucciniosiraceae. En nuestro análisis las siguientes familias corresponden a clados bien definidos con alto soporte estadístico: Pucciniaceae, Phakopsoraceae, Phragmidiaceae, Pileolariacea y Mikronegeriaceae, aunque en algunos casos existen especies que no se agrupan en los clados representativos de dichas familias y que por tanto requieren un tratamiento taxonómico especial, siendo evidente esta situación con algunas especies del género Puccinia. Las familias Uropyxidaceae, Raveneliaceae y Chaconiaceae se presentan como polifiléticas, mientras que Pucciniosiraceae es claramente un taxón redundante con Pucciniaceae. Estas conclusiones del análisis concuerdan con lo encontrado por Aime (2006) quien utilizó un grupo diferente de hongos roya y la combinación de dos regiones ribosomales para su estudio.
El linaje Melampsoraceae sensu lato está conformado por especies de royas que cuando son heteroicas desarrollan su estado aecial sobre plantas gimnospermas (Wingfield et al. 2004). Las familias Coleosporiaceae y Cronartiaceae definidas por Cummins & Hiratsuka (2003), se muestran como clados bien soportados en nuestro análisis, mientras que la familia Pucciniastraceae es polifilética y Melampsoraceae se presenta como un taxón independiente, que requiere un análisis posterior, tal como se mencionó anteriormente.
A continuación se realiza una discusión basada en las familias establecidas por Cummins & Hiratsuka (2003) con relación a los hallazgos de los análisis filogenéticos y morfológicos efectuados en este estudio y con énfasis en los especímenes colectados en la zona andina de Colombia.
Pucciniaceae Chevall
Esta familia comprende el mayor número de hongos roya del orden, con cerca de 7 000 especies y 16 géneros, los géneros Puccinia y Uromyces fueron los más numerosos con 3 000 y 600 especies, respectivamente (Kirk et al. 2001, Cummins & Hiratsuka 2003). El clado que representa esta familia en el análisis filogenético aparece dividido en dos subgrupos (IA y IB), los que a su vez presentan indistintamente especies de Puccinia y Uromyces colectadas en Colombia y en otras regiones del mundo, y se demostró la naturaleza polifilética de dichos géneros. Esta situación fue confirmada por dos estudios recientes realizados con base en secuencias de los genes nucleares EF 1α y β-tub (Van Der Merwe et al. 2007) y de la subunidad grande del ADNr (Maier et al. 2007), en los cuales se analizó un alto número de especies y se determinó que la principal característica morfológica empleada para diferenciar dichos géneros (número de células presentes en las teliosporas), no corresponde a un carácter filogenéticamente informativo. En dichos estudios se encontró que efectivamente las especies tipo de estos géneros (P. graminis y U. appendiculatus) representan linajes diferentes, situación que coincide en esta investigación con la ubicación de U. appendiculatus en un subgrupo diferente a las especies de Puccinia colectadas sobre plantas de la familia Poaceae (P. coronata, P. striiformis), las cuales están estrechamente relacionadas con P. graminis (Maier et al. 2007). En el subgrupo IA, se incluye además un representante del género Cumminsiella y de la especie anamórfica Aecidium kalanchoe. El primero se diferencia del género Puccinia por presentar dos poros por cada célula de las teliosporas, sin embargo la validez filogenética de este género requiere del análisis de un mayor número de especies.
Una confirmación importante de este estudio con respecto a los trabajos de Wingfield et al. (2004), Aime (2006) y Van Der Merwe et al. (2007), corresponde a la redundancia de las familias Pucciniaceae y Pucciniosiraceae. Según Buriticá & Hennen (1980), las royas de esta última familia son derivadas principalmente de especies de ciclo largo del complejo Puccinia-Uromyces, géneros que también resultaron polifiléticos. interesantemente, estos autores en su monografía de Pucciniosireae, sugerían la necesidad de tratar esta familia como una tribu dentro de Pucciniaceae, caracterizada por presentar royas autoicas con ciclo reducido, telioporas en cadena que asemejan aeciosporas y que frecuentemente presentan células intercaladas o estructuras similares a pedicelos. La ubicación de las especies recolectadas pertenecientes a la tribu Pucciniosireae en la parte superior del árbol, sugiere que estas royas son uno de los grupos más evolucionados dentro de los Uredinales incluidos en este análisis, lo cual también es evidenciado por el alto nivel evolutivo de sus hospedantes (ej. Asteraceae: Chardoniella spp). La separación de las especies del género Pucciniosira recolectadas en nuestro estudio con respecto a la especie cuya secuencia se obtuvo del GenBank (P. pallidula) puede ser explicada por las diferencias evidentes entre sus hospedantes, que para nuestro caso corresponden a plantas pertenecientes a los género Solanum y Cestrum endémicas de las zonas altoandinas, mientras que la especie P. pallidula es parásita de Triumfetta semitriloba, una planta de origen más ancestral. De otra parte, la similitud morfológica entre estas royas, puede ser explicada por un proceso de evolución convergente, que hace necesario redefinir los caracteres morfológicos que definen el género Pucciniosira sensu stricto.
Por fuera del clado se ubicó un representante del género Gymnosporangium (Pucciniaceae) el cual tradicionalmente se ha incluido en esta familia con base en la morfología de su espermogonio, aunque presenta otras características que son únicas y que claramente lo diferencian de los demás miembros de Pucciniaceae: estado telial de consistencia gelatinosa desarrollado sobre gimnospermas y estado aecial tipo Roestelia sobre dicotiledóneas frecuentemente de la familia Rosaceae (Cummins & Hiratsuka 2003).
Interesantemente, la especie Puccinia podophylli se presentó asociada con G. juni-peri-virginianae, aunque con un débil soporte estadístico. Este grupo a su vez, conformó un clado con dos especies del género anamórfico Uredo (U. baruensis y U. chusqueae), además de la especie Kweilingia divina, un miembro de la familia Phakopsoraceae. La formación de dicho clado no presenta ninguna justificación desde el punto de vista morfológico y su relación requiere ser redefinida con un mayor número de representantes de los géneros involucrados. De especial interés resultó el hecho que U. chusqueae presentó una alta relación con K. divina, dada la gran afinidad filogenética de sus hospedantes de la familia Poaceae: Guadua angustifolia para K. divina y Chusquea sp. para U. chusqueae.
Finalmente, del análisis filogenético de los miembros de la familia Pucciniaceae recolectados en este estudio, se presentan situaciones puntuales que sin duda brindarán un aporte fundamental desde la perspectiva del neotrópico a la construcción de un sistema taxonómico “más natural” de los hongos roya, pero para lo cual deben ser colectados un mayor número de especímenes. Entre dichas situaciones se destaca la localización de Puccinia oxalidis y P. pittieriana en la posición apical del clado I y la localización de P. smilacis y P. physalidis por fuera del grupo que representa la familia Pucciniaceae, pero en asocio con Gymnoconia peckiana y Uredo zeugites, respectivamente, así como la estrecha asociación entre la especie Maravalia guianensis y Puccinia peperomiae, lo que sin duda merece un análisis futuro, pues morfológicamente estas especies son bastante diferentes.
Phakopsoraceae (Arthur) Cummins & Y. Hiratsuka
Esta familia presenta 13 géneros teliomórficos (Cummins & Hiratsuka 2003) y al menos 10 formas anamórficas (Buriticá & Hennen 1994) de royas en gran diversidad de plantas mono y dicotiledóneas. Se caracterizan por presentar espermogonios del Grupo VI, teliosporas sésiles embebidas en el tejido del hospedante y formadas sobre teliosoros compuestos de una corteza de teliosporas con dos o más células de profundidad (Cummins & Hiratsuka 2003). La familia estuvo representada en el análisis por miembros de los géneros Phakopsora, Batistopsora, Arthuria y Kweilingia. Los tres primeros géneros conformaron el clado IV que presentó un alto soporte en el dendrograma, dentro del cual se ubicó el especímen colectado Arthuria sp., mientras que Kweilingia lo hizó en el clado II. La situación de Kweilingia ya fue discutida anteriormente. En este caso su ubicación por fuera del clado de la familia Phakopsoraceae conduce a inferir que la asociación taxonómica de este género es incierta, aunque su posición en el dendrograma, no soporta la anotación de Thirumalachar & Narasimhan (1951) en el sentido que este hongo no debería ser considerado como una roya, sino como un miembro de los Auriculares. Una interesante evaluación que se deriva de este análisis, es la necesidad de incluir en un estudio posterior royas de esta familia que parasitan pastos tales como aquellas del género Dasturella, pues es posible que dichas especies también se ubiquen por fuera del clado que representa Phakopsoraceae sensu stricto, ya que sus características morfológicas son muy diferentes a aquellas propias de los demás miembros de esta familia.
De especial interés resultaron las diferencias en las secuencias encontradas entre P. pachyrhizi y P. meibomiae, comúnmente conocidas como la roya asiática y americana de la soya, respectivamente, y alrededor de cuya clasificación existe una polémica mundial (Frederick et al. 2002). Nuestros resultados confirman que estas royas no representan la misma especie y que el especímen colectado en Colombia corresponde a P. meibomiae. Morfológicamente esta diferenciación ha sido soportada por estudios basados en sus teliosoros (Ono et al. 1992) y en los trabajos moleculares adelantados por Frederick et al. (2002) y Posada (2008), quienes encontraron que éstas presentan una similitud en las secuencias de las regiones ITS del ADNr de tan sólo 80%, y que su genoma mitocondrial presenta diferencias en tamaño y % G+C (P. pachyrhizi: 31.8 kb, 34.6% vs P. meibomiae: 32.5 kb, 34.9%). Finalmente es importante anotar que el análisis de MP ubicó a esta familia en estrecha relación con Prospodium lippiae, un miembro de la familia Uropyxidaceae caracterizado por formar espermogonios subcuticulares del grupo Phakopsoraceae, pero cuyas teliosporas son claramente diferentes: pediceladas con dos células y con presencia de apéndices basales. Esta relación requiere de un análisis posterior con un mayor número de representates del género Prospodium.
Phragmidiaceae Corda
Esta familia está representada por diez géneros de royas autoicas que parasitan casi exclusivamente plantas de la familia Rosaceae y se caracterizan por producir espermogonios del grupo IV (tipos 6, 8, 10 ó 11) con teliosporas pediceladas con uno a varios septos transversales y desarrolladas sobre telios erumpentes (Cummins & Hiratsuka 2003). Los análisis filogenéticos recientes (Maier et al. 2003, Aime 2006) han confirmado el carácter monofilético de la familia y la cercanía evolutiva entre los géneros Kuehneola y Phragmidium. En nuestro análisis la condición filogenética de esta familia fue igualmente confirmada con base en secuencias de los géneros Gymnoconia, Frommeella, Kuehneola y Trachyspora; sin embargo, el hecho que ninguna especie recolectada de esta familia en Colombia pudo ser secuenciada, hace necesario su abordaje en un futuro estudio. De gran interés será el análisis de diferentes especies del género Gerwasia, el cual afecta plantas del género Rubus, es típicamente tropical y presenta teliosporas de una sola célula, que difieren ampliamente de los demás miembros de esta familia.
Coleosporiaceae Dietel
Esta familia es una de las representantes del suborden Melampsorineae (Aime 2006) que sistemáticamente en los diferentes estudios basados en secuenciación del ADN, se presenta como un linaje filogenético bien soportado, pero cuyos límites familiares no están claramente definidos. Esta situación es evidente cuando se consideran los resultados de los análisis con los dos géneros de la familia Coleosporiaceae incluidos en nuestro estudio: Coleosporium y Chrysomyxa. En este caso, ambos se ubican en el clado III y se presentan individualmente bien soportados, pero con Chrysomyxa más relacionado con los géneros Cronartium y Endocronartium de la familia Cronartiaceae, que con Coleosporium. Esta situación soporta los hallazgos de Maier et al. (2003) y Wingfield et al. (2004) en el sentido que la monofilia de la familia no pudo ser definida y conduce a interpretar que las diferencias morfológicas que se presentan entre ambos géneros: germinación de teliosporas interna (basidiación interna) (Coleosporium) vs germinación de teliosporas que producen basidios externamente (Chrysomyxa), deben ser consideradas más detalladamente en los estudios de este grupo de royas.
Chaconiaceae Cummins & Y. Hiratsuka y Mikronegeriaceae Cummins & Y. Hiratsuka
Morfológicamente la familia Chaconiaceae se caracteriza por presentar espermogonios del grupo VI (tipos 5 ó 7), uredosporas generalmente equinuladas y teliosporas unicelulares, lateralmente libres, sésiles ó pediceladas. Cummins & Hiratsuka (2003) reconocen diez géneros dentro de esta familia, aunque Ono & Hennen (1983) no consideran los géneros Achrotelium, Botryorhiza, Chaconia y Maravalia como pertenecientes a ésta, debido a la presencia de teliosporas pediceladas. Es claro de este estudio y de aquellos adelantados por Wingfield et al. (2004) y Aime (2006) que la válidez taxonómica de la familia Chaconiaceae no es soportada filogenéticamente, siendo evidente la necesidad de clarificar la afinidad de algunos de sus géneros con la familia Mikronegeriaceae; familia ésta que sólo estuvo representada por la especie Chrysocelis muechlenbeckiae y cuya ubicación en el dendrograma correspondió a un clado compartido con Chrysocyclus cestri (Pucciniaceae) y dos especies de Ravenelia (Raveneliaceae).
La afinidad del género Hemileia con esta familia es igualmente problemática, pues ya desde la mitad del siglo pasado Thirumalachar & Mundkur (1949) habían sugerido que este taxón estaba relacionado con el género Blastospora, hoy en día considerado de la familia Mikronegeriaceae (Cummins & Hiratsuka2003). Esta cercana asociación fue recientemente confirmada por Aime (2006), quien con base en análisis del ADNr sugiere que Hemileia y al menos una especie del género Maravalia (M. cryptostegiae) deberían ser ubicadas en Mikronegeriaceae, la que además representa un grupo ancestral dentro del orden Uredinales. Esta situación se vió reflejada en nuestro estudio mediante MP. El análisis además no permitió establecer una cercana relación entre H. vastatrix (agente causal de la roya del café) y H. colombiana (roya de Apocynaceae); así como tampoco fueron definidas afinidades entre éstas royas y las otras especies estudiadas de la familia Chaconiacae (Olivea scitula y Maravalia guianensis); pues la primera especie aparece en posición basal en el dendrograma, mientras que M. guianensis se ubicó en el clado IA, que representa un linaje de la familia Pucciniaceae.
A partir de los resultados de esta investigación, que incluyó un alto número de hongos roya representantes de diferentes géneros, se propone priorizar la continuación de este estudio con base en el análisis filogenético de los siguientes taxones:Gerwasia, Hemileia, Phragmidium, Prospodium, Puccinia y Uromyces. Dichos grupos contienen gran cantidad de royas presentes en el trópico que requieren ser estudiadas más detalladamente.
Agradecimientos
Esta investigación se realizó gracias al apoyo económico de la dirección de investigaciones de la Universidad Nacional de Colombia sede Medellín a través del proyecto 20201005428. La identificación taxonómica de los hospedantes se realizó con apoyo de Jorge Pérez del Herbario Medel y el análisis filogenético con la colaboración de Andrés López Rubio y Sandra Uribe Soto del Grupo de sistemática molecular UNAL-MED. Se agradece a Mauricio Salazar Yepes por la revisión crítica del manuscrito.
Referencias
Aime, M.C. 2006. Toward resolving family-level relation-ships in rust fungi (Uredinales). Mycoscience 47: 112-122. [ Links ]
Aime, M.C., M.P. Brandon, D.A. Henk, E.M. Frieders, R.H. Nilson, M. Piepenbring, D.J. Mclaughlin, L.J. Szabo, D. Begerow, J.P. Sampaio, R. Bauer, M. Weib, F.Y. Oberwinkler & D. Hibbert. 2006. An overview of the higher level classification of Pucciniomyco-tina based on combined analyses of nuclear large and small subunit rDNA sequenses. Mycologia 98: 896-905. [ Links ]
Bauer, R., D. Begerow, J.P. Sampaio, M. Weiß & F. Oberwinkler. 2006. The simple-septate basidiomyce-tes: a synopsis. Mycol. Progr. 5: 41-66. [ Links ]
Blackwell, M., D. Hibbert, J.W. Taylor & J.W. Spatafora. 2006. Research Coordination Networks: a phylogeny or kingdom Fungi (Deep Hypha). Mycologia 98: 829-837. [ Links ]
Buriticá, P. 1991. Familias del orden Uredinales con ciclo de vida completamente reducido. Rev. Acad. Col. Cienc. 18: 131-148. [ Links ]
Buriticá, P. 1994. Cambios taxonómicos y nuevos registros de Uredinales de la flora andina. Rev. i.C.N.E. 5: 173-190. [ Links ]
Buriticá, P. 1999a. Familia Phakopsoraceae (Uredinales) en el Neotrópico III, géneros Batistopsora y Phakopsora. Rev. Acad. Col. 23: 272. [ Links ]
Buriticá, P. 1999b. Familia Phakopsoraceae (Uredinales) en el Neotrópico IV, Géneros Cropssopsora, Cerotelium, Phragmidiella y Catenulopsora. Rev. Acad. Col. 23: 407. [ Links ]
Buriticá, P. 2000. Adaptación al ambiente de Uredinales neotropicales. O Biol. 62: 127-141. [ Links ]
Buriticá, P. 2001. Descubriendo ancestros de los Uredina-les. Rev. Acad. Col. Cien. 25: 395-401. [ Links ]
Buriticá, P. 2003a. Centros naturales de diversificación en el orden Uredinales (Fungi, royas). Rev. Fac. Nal. Agr. Medellín 56: 1999-2019. [ Links ]
Buriticá, P. 2003b. Estado del conocimiento universal sobre el orden Uredinales (Fungi, royas). Rev. Fac. Nal. Agr. Medellín 56: 1813-1838. [ Links ]
Buriticá, P. & J. Hennen. 1980. Familia Phakopsoraceae (Uredinales). Géneros anamórficos y teliomórficos. Rev. Acad. Colomb. Cienc. Ex. Fis. Nat. 19: 47-62. [ Links ]
Buriticá, P. & J. Hennen. 1980. Pucciniosireae (Uredi-nales, Pucciniaceae). Flora Neotropica Monograph 24: 1-50. [ Links ]
Buriticá, P. & J. Hennen. 1994. Familia Phakopsoraceae (Uredinales). 1. Géneros anamórficos y teliomórficos. Rev. Acad. Colomb. Cienc. Ex. Fis. Nat. 19:47-62. [ Links ]
CABI, CBS & Landcare Research. 2008. Index Fungorum. (Consultado: Diciembre 2007, http://www.indexfungorum.org). [ Links ]
Cummins, G. 1940. The genus Prospodium (Uredinales). Lloydia 3: 1-78. [ Links ]
Cummins, G. 1971. The rust fungi of cereals, grasses and bamboos. Springer-Verlag, Nueva York, EEUU. [ Links ]
Cummins, G. 1978. Rust fungi on legumes and composites in North America. University of Arizona Tucson, Tucson, EEUU. [ Links ]
Cummins, G. & Y. Hiratsuka. 1983. Illustrated genera of rust fungi. American Phytophatological Society, San Pablo, EEUU. [ Links ]
Cummins, G. & Y. Hiratsuka. 1991. Illustrated genera of rust fungi. American Phytophatological Society, San Pablo, EEUU. [ Links ]
Cummins, G. & Y. Hiratsuka. 2003. Illustrated general of rust fungi. American Phytophatological Society, San Pablo, EEUU. [ Links ]
Dietel, P. 1928. Hemibasidii (Ustilaginales and Uredina-les), p 24-98. In A. Engler & K. Plantl (eds). Die Natürlichen Pflanzenfamilien, vol 2. Engelmann, Leipzig, Alemania. [ Links ]
Durrieu, G. 1980. Phylogeny of Uredinales on Pinaceae. Rep. Tottori Mycol. inst. 18: 283-290. [ Links ]
Felsenstein, J. 1985. Confidence limits on phylogenies: an approach using the bootstrap. Evolution 39: 783-791. [ Links ]
Frederick, R.D., C.L. Snyder, G.L. Peterson & M.R. Bonde. 2002. Polymerase chain reaction assays for the detection and discrimination of the soybean rust pathogens Phakopsora pachyrhizi and P. meibomiae. Phytopathology 92: 217-227. [ Links ]
Gaumann, E. 1949. Die Pilze. Grundzüge ihrer Entwicklungsgeschichte und Morphologie. Birkhauser, Basilea, Suiza. [ Links ]
Guadet, J., J. Julien & J. Francois. 1989. Phylogeny of some Fusarium species, as determined by largesubunit rRNA sequence comparison. Mol. Biol. Evol. 6: 227-242. [ Links ]
Hahn, M. 2000. The rust fungal, p. 267-306. In J. Krons-tand (ed.). Fungal pathology. Kluwer, Holanda. [ Links ]
Hawksworth, D.L., P.M. Kirk, B.C. Sutton & D.N. Pegler. 2001. Ainswork & Bisby´s dictionary of the fungi. 8th ed. int. Mycol. inst., CAB int., Egham, Reino Unido. [ Links ]
Hennen, J., M. Hennen & M. Figueiredo. 1982. indice das ferrugens (Uredinales) do Brasil. Arq. inst. Biol. (Sao Paulo) 49: 1-201. [ Links ]
Hennen, J., M. Figueiredo, A. De Carvalho & P.G. Hen-nen. 2005. Catalogue of the species of plant rust fungi (Uredinales) of Brazil. (Consultado: Octubre 2007, http://www.jbrj.gov.br/publica/uredinales/Brazil_Catalogue1drevisado.pdf). [ Links ]
Hiratsuka, Y. & N. Hiratsuka. 1980. Morphology of spermogonia and taxonomy of rust fungi. Rep. Tottori Mycol. inst. 18: 257-268. [ Links ]
Hopple, J. & R. vilgalys. 1999. Phylogenetic relationships in the mushroom genus Coprinus and darkspored allies based on sequence data from the nuclear gene coding for the large ribosomal subunit RNA: divergent domains, outgroups, and monophyly. Mol. Phylogenet. Evol. 13: 1-19. [ Links ]
Kirk, P.M., P.F. Cannon, J.C. David & J.A. Stalpers. 2001. Dictionary of the fungi. CABi, Wallingford, Reino Unido. [ Links ]
The New York Botanical Garden Herbarium. 2003. Catalog of Rust Types. (Consultado: Abril 2008, http://www.nybg.org/bsci/hcol/rust). [ Links ]
Maier, W., D. Begerow, M.Y. Wei & F. Oberwinkler. 2003. Phylogeny of the rust fungi: An approach using nuclear large subunit ribosomal DNA sequences. Can. J. Bot. 81: 1-12. [ Links ]
Maier, W., B.D. Wingfield & M. Mennicken. 2007. Polyphyly and two emerging lineages in the rust genera Puccnia and Uromyces. Mycol. Res. 176-185. [ Links ]
Ono, Y., P. Buriticá & J.F. Hennen. 1992. Delimitation of Phakopsora, Physopella and Cerotelium and their species on Leguminosae. Mycol. Res. 96: 825-850. [ Links ]
Ono, Y. & J.F. Hennen. 1983. Taxonomy of the Chaconiaceous genera (Uredinales). Trans. Mycol. Soc. Jpn. 24: 369-402. [ Links ]
Pardo-Cardona, v. 1999. Notas técnicas especies de Ure-dinales (Royas) con rara formación del estado teliomórfico en Colombia. Rev. Fac. Nal. Agr. Medellín 52: 755-764. [ Links ]
Pardo-Cardona, v. 2001. Historia, estado actual y perspectivas de la investigación de los Uredinales en Colombia. Rev. Fac. Nal. Agr. Medellín 54: 1333-1350. [ Links ]
Posada, M.L. 2008. Soybean rust, a rising star in phytopatho-logy. (Consultado: Abril 2008, http://www.osti.gov/bridge/servlets/purl/860744-7ClNx8/860744.PDF). [ Links ]
Salazar, M. 2002. Uredinales (royas) en la zona cafetera colombiana. Tesis Maestría, Universidad de Caldas, Manizales, Colombia. [ Links ]
Salazar, M., V. Pardo-Cardona & P. Buriticá. 2007. Especies de Colombia, Ecuador y Perú pertenecientes al género Gerwasia Raciborski del orden Uredinales. Caldasia 29: 105-120 [ Links ]
Sugiyama, J. 1998. Relatedness, phylogeny, and evolution of the fungi. Mycoscience 39: 487-511. [ Links ]
Swofford, D.L. 1998. PAUP: Phylogenetic analysis using parsimony (* and other methods). versión: 4. Sinauer Associates, Sunderland, EEUU. [ Links ]
Thirumalachar, M.J. & B.B. Mundkur. 1949. Genera of rust ii. ind. Phytopathol. 2: 65-101. [ Links ]
Thirumalachar, M.J. & M.J. Narasimhan. 1951. Critical notes on some plant rusts. iii. Sydowia 5: 476-483. [ Links ]
Van Der Merwe, M., L. Ericson, J. Walker, P.H. Thrall & J.J. Burdon. 2007. Evolutionary relationships among species of Puccinia and Uromyces (Pucciniaceae, Uredinales) inferred from partial protein coding gene phylogenies. Mycol. Res. 111: 163-175. [ Links ]
Vogler, D. & T. Bruns. 1998. Phylogenetic relationships among the pine stem rust fungi (Cronartium and Peridermium spp.). Mycologia 99: 244-257. [ Links ]
Wingfield, B., L. Ericson, T. Szaro & J. Burdon. 2004. Phylogenetic patterns in the Uredinales. Australas. Plant Pathol. 33: 327-335. [ Links ]
Zuluaga, C., P. Buriticá & M. Marín. 2009. Generalidades de los Uredinales (Fungi: Basidiomycota) y de sus relaciones filogenéticas. Acta Biol. Colomb. 14: 39-54 [ Links ]
Correspondencia a: Catalina Zuluaga & Mauricio Marín. Universidad Nacional de Colombia sede Medellín, Laboratorio de Biología Celular y Molecular, Cra 64 x Calle 65, Autopista Norte, Medellín, Colombia; catazuluaga81@gmail.com, mamarinm@unal.edu.co
Pablo Buriticá. Universidad Nacional de Colombia sede Medellín, Departamento de Ciencias Agronómicas, Cra 64 x Calle 65, Autopista Norte, Medellín, Colombia; pburitica@unal.edu.co
Recibido 16-IV-2010. Corregido 10-IX-2010. Aceptado 26-X-2010.
1.Universidad Nacional de Colombia sede Medellín, Laboratorio de Biología Celular y Molecular, Cra 64 x Calle 65, Autopista Norte, Medellín, Colombia; catazuluaga81@gmail.com, mamarinm@unal.edu.co
2.Universidad Nacional de Colombia sede Medellín, Departamento de Ciencias Agronómicas, Cra 64 x Calle 65, Autopista Norte, Medellín, Colombia; pburitica@unal.edu.co
Dirección para correspondencia
Abstract
Phylogenetic analysis of rust fungi (Uredinales) from the Colombian Andean region using 28S ribosomal DNA sequences. Rust fungi (Uredinales, Basidiomycetes) are one of the most diverse and economically important plant-obligated parasites. Taxonomy of this group has been under revision during the last years using molecular techniques to define phylogenetic relationships. In this study we evaluated the phylogenetic affinities of a group of 40 rust fungi obtained from different plants in the Colombian Andean region using sequence analysis of the 28S ribosomal DNA, specifically D1/D2 domains. Comparisons were undertaken with sequences of rust fungi from around the world deposited in the GenBank database. An alignment of sequences was used to build a phylogenetic tree through Maximum parsimony analysis. Our results support the taxo- nomical validity of families Pucciniaceae, Phakopsoraceae, Phragmidiaceae, Pileolariaceae, Mikronegeriaceae, Coleosporiaceae and Cronartiaceae, while Pucciniosiraceae represents redundant taxa with Pucciniaceae. The analyses indicated that Uropyxidaceae, Raveneliaceae, Chaconiaceae and Pucciniastraceae correspond to poly- phyletic families. Melampsoraceae appear to be a basal taxon to the Uredinales. information obtained in this study will be useful to incorporate a higher number of sequences from tropical rust fungi within global efforts to redefine the taxonomy of order Uredinales. Additionally, we propose to give priority to future phylogenetic studies of taxa: Gerwasia, Hemileia, Phragmidium, Prospodium, Puccinia and Uromyces, genera that include a high number of rust fungi from the tropics. Rev. Biol. Trop. 59 (2): 517-540. Epub 2011 June 01.
Key words: maximum parsimony, rDNA, rust fungi, sequence analyses.
Resumen
Los hongos roya (Uredinales, Basidiomycetes) representan uno de los grupos de fitoparásitos más diversos y con mayor importancia económica agrícola mundial. Su taxonomía se ha basado en el estudio de caracteres morfológicos, que resulta en muchos casos en la formación de taxones polifiléticos. Sin embargo, en los últimos años se han tratado de incorporar herramientas moleculares que conduzcan a la generación de sistemas de clasificación basados en afinidades evolutivas. Este trabajo pretendió aumentar la base del conocimiento sobre la uredobiota tropical, mediante el estudio de características morfológicas y filogenéticas de un grupo de royas de los Andes de Colombia. Para esto se secuenció parte de la región 28S del ADNr y se realizó un análisis de agrupamiento mediante Máxima parsimonia. Los resultados confirmaron la validez de las familias Pucciniaceae, Phakopsoraceae, Phragmidiaceae, Pileolariaceae, Mikronegeriaceae, Coleosporiaceae y Cronartiaceae, mientras que Pucciniosiraceae es un taxón redundante con Pucciniaceae. Por su parte, Uropyxidaceae, Raveneliaceae, Chaconiaceae y Pucciniastraceae se muestran como familias polifiléticas. Aparentemente Melampsoraceae se presenta como un taxón basal al grupo. La información que se deriva de este estudio se espera sea incorporada en los estudios mundiales que buscan redefinir el sistema taxonómico de los hongos roya.
Palabras clave: ADNr, hongos roya, máxima parsimonia, puccinia, secuenciación.
Los hongos roya (Urediniomycetes, Uredinales) constituyen uno de los grupos de hongos más numeroso, diverso y de amplia distribución mundial (Buriticá 2003a); son parásitos obligados (holobiótrofos) de un amplio rango de plantas incluidas helechos, coníferas y angiospermas, con las cuales han coevolucionado, que adaptan su ciclo de vida a las condiciones ecológicas del hábitat de sus hospedantes (Buriticá 2001, Buriticá 2003b, Cummins & Hiratsuka 2003, Zuluaga et al. 2009). Los Uredinales son conocidos como royas por la inducción de pústulas que contienen esporas con apariencia de un polvillo herrumbroso sobre los tejidos de sus hospedantes; sin embargo, también pueden causar hipertrofias e hiperplasias, escobas de bruja y formación de pseudoflores (Cummins & Hiratsuka 2003).
El orden Uredinales está conformado por 13 familias, 163 géneros y unas 7 000 especies (Hawksworth et al. 2001); aunque se estima que el grupo puede contener de 20 000 a 24 000 especies (Buriticá 2003b). Recientemente, Bauer et al. (2006) en su estudio de los Basidiomycetes con septos simples, sugirieron renombrar las categorías suprafamiliares en que se ubican los hongos roya como orden Pucciniales de la clase Pucciniomycetes. Los hongos roya pueden producir hasta cinco estados espóricos que se designan como: espermogonio (espermacios e hifas receptivas) (O), aeciospora (I), uredospora (II), teliospora (III) y basidiospora (IV) (Hahn 2000). Cada estado espórico es morfológica y funcionalmente diferente dentro del ciclo de vida de las especies de royas (Hawksworth et al. 2001, Cummins & Hiratsuka 2003).
La clasificación de los Uredinales a nivel genérico y supragenérico ha sido basada casi exclusivamente en la morfología de los telio-soros y teliosporas. Inicialmente dos familias fueron definidas por las características morfológicas de sus teliosporas: Melampsoraceae con teliosporas no pediceladas (teliosoros subepidermales, cubiertos) y Pucciniaceae con teliosporas pediceladas (teliosoros erumpentes) (Dietel 1928). Posteriormente, Gaumann (1949) adicionó las familias Pucciniastraceae (teliosoros inmersos), Cronartiaceae (teliosoros columnares), Chrysomyxaceae (teliosoros cupulares) y Coleosporiaceae (basidio interno). Cummins & Hiratsuka (1983) propusieron la definición de 14 familias para el orden Uredinales, las cuales luego redujeron a 13, una vez unidas las familias Raveneliaceae y Sphaerophragmiaceae (Cummins & Hiratsuka 2003).
La taxonomía de hongos se ha fundamentado tradicionalmente en el empleo de caracteres morfológicos. En muchos casos estas características son variables, que producen información insuficiente o poco precisa que conduce a la generación de clasificaciones no naturales. En las últimas décadas, la secuenciación de regiones ribosomales y funcionales ha jugado un papel fundamental en la inferencia de las relaciones evolutivas entre individuos y grupos de individuos (Sugiyama 1998, Blackwell et al. 2006). Sin embargo, el número de estudios que emplean estas herramientas moleculares para la realización de estudios taxonómicos en hongos roya es muy reducido, en comparación con aquellos realizados en otros grupos de hongos (Zuluaga et al. 2009), siendo son los más destacados aquellos realizados por Maier et al. (2003, 2007), basados en la secuenciación de una porción de la región 28S del ADNr en hongos roya recolectados principalmente en Europa y que pusieron de manifiesto que los géneros Puccinia, Pucciniastrum, Thekopsora y Uromyces son polifiléticos, mientras que Chrysomyxa, Coleosporium, Cronartium, Gymnosporangium, Melampsora, Phragmidium y Tranzschelia, representan taxones monofiléticos. La condición polifilética de los géneros Puccinia y Uromyces fue confirmada posteriormente por van der Merwe et al. (2007) quienes usaron análisis de secuencias de los genes del factor de elongación 1α y β-tubulina 1. Un estudio similar fue realizado por Wingfield et al. (2004), pero mediante análisis de secuencias de la subunidad pequeña del ADNr en 64 especies de 12 familias de royas; en este caso se encontró que los géneros que presentan estados aeciales sobre gimnospermas están filogenéticamente distantes de los hongos roya que desarrollan dicho estado sobre plantas angiospermas; además se determinó que la condición de autoicismo/heteroicismo no representa un carácter taxonómico válido y que familias como Pucciniaceae y Pucciniastraceae representan taxones polifiléticos.
Aime (2006) utiliza la estrategia de combinar datos de ambas subunidades ribosomales, al realizar un estudio tendiente a evaluar el soporte filogenético de las familias del orden Uredinales propuestas por Cummins & Hiratsuka (2003) con base en caracteres morfológicos. De las trece familias propuestas, ocho (Coleosporiaceae, Melampsoraceae, Mikronegeriaceae, Phakopsoraceae, Phragmidiaceaeae, Pileolariaceae, Pucciniaceae y Raveneliaceae) están bien soportadas por el análisis basado en secuencias, mientras que tres son redundantes (Cronartiaceae, Pucciniastraceae y Pucciniosi-raceae), y en dos de ellas, su condición no pudo ser definida (Chaconiaceae y Uropyxidaceae).
A pesar del alto número de especies de royas presentes en los trópicos, el nivel de conocimiento que se tiene de estos hongos en esta región es incipiente, tanto desde el punto de vista biológico como en lo relacionado a su clasificación taxonómica. Esta situación contrasta con la gran importancia económica que presentan algunas royas en diversos agroecosistemas tropicales y con el potencial bioprospectivo de especies que podrían ser utilizadas como biorreguladores de plantas arvenses. Una de las regiones neotropicales de las que se posee menor conocimiento sobre este grupo de organismos, es la zona andina que comprende una franja altitudinal entre 2 000 y 4 600m.s.n.m, nicho ecológico que ofrece condiciones físicas y biológicas muy particulares, y específicamente para el caso de hongos roya incluye fundamentalmente especies con ciclos de vida reducido, poco abordadas en los estudios micológicos mundiales que utilizan herramientas moleculares (Zuluaga et al. 2009), aunque parcialmente evaluadas en estudios morfológicos (Buriticá 1991, Buriticá 1994, Buriticá 2000, Pardo-Cardona 2001, Salazar 2002, Buriticá 2003a).
En esta investigación se llevo a cabo una recolección de hongos roya procedentes de plantas cultivables y silvestres de diversas regiones de la zona andina de Colombia, para el estudio de sus características morfológicas y relaciones filogenéticas, como una estrategia para aumentar el nivel de conocimiento que se posee de este grupo de hongos en el trópico, así como para evaluar las hipótesis taxonómicas recientemente apoyadas en estudios moleculares sobre el carácter filogenético de las diferentes familias tradicionalmente propuestas dentro del orden Uredinales.
Materiales y métodos
Recolección de muestras: Las muestras fueron recolectadas en diferentes regiones de cinco departamentos de la zona andina de Colombia (Antioquia, Boyacá, Cundinamarca, Risaralda y Tolima) (Fig. 1), incluye el sistema de páramos y bosques altoandinos del noroccidente medio antioqueño (Belmira, Yarumal), además de las zonas andinas del suroccidente antioqueño (Caramanta, Tamésis, valparaíso). También se incluyeron muestras de regiones montañosas de los departamentos de Boyacá (Sogamoso, Sora), Cundinamarca (Bojacá, El Rosal, Pacho, Subachoque, Tausa, Villa Pinzón, Zipaquirá) Caldas (Manizales, villa María), Risaralda (Quinchia) y Tolima (Páramo de Letras) (Cuadro 1). Para la obtención de las muestras se realizó un recorrido por vías primarias y secundarias de cada uno los sitios descritos, se evaluó la presencia de plantas con síntomas y signos de royas, ante lo cual se tomaban los órganos y tejidos afectados (generalmente al menos una hoja). De esta forma, cada muestra estaba representada por diferentes pústulas de royas en tejidos de una misma planta y dependiendo de la uredobiota presente en cada sitio de muestreo, el número de especímenes recolectados variaba entre zonas. Cada muestra recolectada fue prensada para evitar su deterioro junto con su respectiva información referente al hospedante y a las características geográficas de la zona. Las muestras fueron llevadas al Herbario MEDEL de la Universidad Nacional de Colombia sede Medellín, para su secado e identificación botánica y los especímenes así procesados fueron depositados en el Museo Micológico de la Universidad Nacional de Colombia Sede Medellín (MMUNM).
Caracterización morfológica: La descripción morfológica de los especímenes recolectados incluyó las siguientes observaciones de las pústulas: posición respecto al tejido del hospedante, color, forma, agrupación y consistencia. De cada estado espórico encontrado se realizaron micropreparados para describir su forma, color, ornamentación, número y posición de poros; dimensiones; tamaño de la pared apical y lateral; presencia, posición, ornamentación y largo de pedicelos; presencia de estructuras estériles como parafisos y peridio. Cada muestra fue comparada con especímenes de referencia ubicados en la colección del MMUNM y la Colección Nacional de Royas de Colombia de la Facultad de Ciencias Agropecuarias. Además se utilizaron las monografías taxonómicas de hongos Uredinales (Cummins 1940, 1971, 1978, Buriticá & Hennen 1980, Hennen et al. 1982, Cummins & Hiratsuka 1991, Buriticá 1991, 1994, 1999 a,b, Pardo-Cardona 1999, Salazar 2002, Hennen et al. 2005, Salazar et al. 2007) y las bases de datos del Index Fungorum (CABI et al. 2008) y del catálogo de especies tipo de hongos roya del Jardín Botánico de New York (The New York Botanical Garden Herbarium 2003).
Extracción de ADN: De cada una de las royas se realizó la extracción de ácidos nucleicos mediante dos metodologías: método convencional CTAB 2X/Fenol/Cloroformo y Kit comercial DNAeasy Plant Mini (Qiagen, CA, EEUU), cuyo procedimiento se basó en las instrucciones del fabricante. En ambos casos se partió de uno o varios soros, que dependen de su tamaño y grado de esporulación, y se toma la menor cantidad de tejido vegetal posible para su ubicación en un tubo eppendorf de 1.8mL. En el método convencional los tubos se colocaron en un recipiente con nitrógeno líquido para proceder a la maceración del tejido en presencia de 200µL del buffer CTAB 2X (CTAB 2%, NaCl 1.4M, EDTA 20mM, Tris-HCl 100mM pH 8.0) y 1% de β-Mercaptoetanol, incubándose a 65°C durante 10min. Luego se separó la fase orgánica mediante 1vol. de fenol:cloroformo (1:1) y se centrifugó a 13 000 rpm por 10min. De acuerdo al grado de pureza del sobrenadante, este procedimiento se repitió, pero con el uso de un sólo vol de cloroformo. Para precipitar los ácidos nucleicos se emplearon 2vol de etanol absoluto y 0.1vol de acetato de sodio 3M, y se colocaron los tubos a -20ºC durante al menos 30min, tiempo después del cual se centrifugó a 13 000 rpm por 15min. El microprecipitado resultante se lavó con etanol al 70% y finalmente se resuspendió en 20µL de agua destilada estéril, para su utilización en las amplificaciones de PCR. La cantidad de ADN obtenida se determinó por espectrofotometría a 260nm de longitud para lo cual se utiliza un espectro Thermo Scientific, Genesys 6 (Waltham, MA, EEUU).
Amplificación y secuenciación del ADNr 28S: Para la PCR se emplearon los cebadores LROR (5’ ACC CGC TGA ACT TAA GC 3’) y LR6 (5’ CGC CAG TTC TGC TTA CC 3’) que amplifican una región del extremo 5’ de la subunidad grande del ADNr que contiene los dominios D1 y D2, ampliamente utilizados para estudios filogenéticos de hongos (Guadet et al. 1989, Hopple & Vilgalys 1999). La amplificación de PCR se realizó en un termociclador T3 (Biometra, Göttingen, Alemania) y consistió de una modificación del programa propuesto por Vogler & Bruns (1998), con una desnaturalización inicial a 94°C por 3min, seguido por 35 ciclos de 94°C por 1.30min, 50°C por 1min, 72ºC por 1min y una extensión final a 72°C por 7min. Las reacciones se realizaron en un volumen total de 25 µL, que contiene 0.5µM de cada cebador, 1U de Taq ADN polimerasa recombinante (Fermentas, Vilnius, Lithuania), 0.2mM de cada dNTP, 1X de buffer de enzima (100mM Tris-HCl pH 8.8, 500mM KCl, 0.8% Nonidet P40), 1.8mM MgCl 2, 1µL de ADN [100 - 1000ng/µL] y agua destilada ésteril. Luego de la amplificación se tomaron 5µL de los productos de reacción para analizarlos por electroforesis en gel de agarosa al 1.5% suplementado con 0.5 µg/mL de bromuro de etidio en buffer de corrido TBE 0.5X (45mM Tris-Borato, 1mM EDTA pH 8.0). La visualización de las bandas amplificadas se realizó bajo luz ultravioleta en un transiluminador automático Bio Doc Analyze (Biometra). Una vez definida la especificidad y tamaño de los productos amplificados, se procedió a su purificación utilizando los kits Wizard PCR Preps ADN Purification System (Promega, Madison, EEUU) y QiAquick PCR Purification Kit (Qiagen, CA, USA) para proceder a su secuenciación directa mediante el sistema Big Dye Terminator Cycle Sequencing Ready Reaction (PE Applied Biosystems, Foster City, EEUU) y su corrido en un secuenciador ABI Prism 3730xl (PE Applied Biosystems) de la compañía Macrogen (Corea del Sur).
Las secuencias obtenidas con cada cebador, fueron editadas mediante el software BioEdit 6.0.6 y Chromas 1.45, se construyeron secuencias consenso y se confirmó su validez por comparación con las bases de datos moleculares, mediante el programa BLASTn (NCBI 2007). Paralelamente, se obtuvieron del GenBank secuencias de la subunidad 28S del ADNr de hongos roya representativos de las 13 familias propuestas por Cummins & Hiratsuka (2003) (Cuadro 2), para su alineamiento con las generadas en este proyecto, mediante el software Clustal W. Como grupos externos de análisis (outgroups) se utilizaron las secuencias de los Basidiomycetes: Septobasidium carestianum Bres. y Eocronartium muscicola Pers., seleccionados con base en los resultados de Maier et al. (2003). El análisis filogenético se realizó utilizando el método de Máxima parsimonia (MP) con búsqueda heurística y TBR (tree-bisection-reconnection) mediante el software PAUP 4.0b10 (Swofford 1998) con base en 1 000 remuestreos y tratando los gaps como quinta base. El soporte de la topología interna del dendrograma fue evaluado mediante análisis de bootstrap con 1 000 remuestreos o iteraciones (Felsenstein 1985).
Resultados
Colección de muestras: En total se identificaron 100 especímenes de hongos roya con base en sus caracteres morfológicos a partir de 238 muestras de hospedantes (Cuadro 1). Del total de muestras identificadas, 25 fueron obtenidas de plantas de la familia Asteraceae y 14 de la familia Solanaceae. Una sola roya fue obtenida de plantas de las familias Alstroemeriaceae, Apiaceae, Apocynaceae, Bromeliaceae,Cannaceae, Cucurbitaceae, Denstaedtiaceae, Liliaceae, Malvaceae, Moraceae y Piperaceae; dos de Betulaceae, Lamiaceae, Malpighiaceaey Oxalidaceae; tres de Convolvulaceae y ver-benaceae; cuatro pertenecieron a Euphorbiaceae y Polygonaceae; seis a Rubiaceae, siete a Rosaceae y nueve a Fabaceae y Poaceae. No fue posible identificar botánicamente una muestra por falta de material (Cuadro 1).
Caracterización morfológica: Las 100 muestras identificadas correspondieron a 61 especies diferentes con la siguiente distribución: dos especies de las familias Pucciniastraceae, Coleosporiaceae, Mikronegeriaceae,Uropixydaceae, Phragmidiaceae; tres especies de Chaconiaceae; cuatro especies de Pucci-niosiraceae y Phakopsoracea; 33 especies de Pucciniaceae y siete muestras correspondieron a estados anamórficos identificados como Uredo sp. y Aecidium sp. En el Cuadro 3 se presentan los resultados de las mediciones de los estados espóricos encontrados en un representante de las 61 especies identificadas. Las dimensiones corresponden al formato: medición mínima - medición máxima (promedio;desviación éstandar). Las descripciones para cada especie se encuentran disponibles en el material anexo asociado a este manuscrito.
Amplificación y secuenciación de ADNr28S: Con la metodología de extracción de ADN convencional se obtuvieron 68 amplicones. En aquellas muestras en las que luego de varios intentos de amplificación por PCR no fue posible obtener el fragmento esperado, se procedió a la extracción de ADN mediante el kit comercial de Qiagen, se obtuvieron 32 amplicones adicionales. La secuenciación del fragmento amplificado se realizó en ambas direcciones en reacciones individuales con cada uno de los cebadores utilizados en el PCR. Luego de varios intentos, se obtuvieron ambas secuencias en 40 de las royas recolectadas, no se incluyeron en el análisis posterior las royas para las que se generaron secuencias en un sólo sentido, pues esto implicaba reducir el número de sitios para el análisis de MP. Una vez editadas las secuencias y construidos los consensos, se determinó que el tamaño de este fragmento oscilaba entre 1 080 y 1 170 pb, según la especie de roya. Pero, con el fin de homogenizar los extremos de las secuencias, fue necesaria su edición, obteniéndose entre 1 000 y 1 100 pb. Las secuencias fueron depositadas en el GenBank y sus números de accesión se registran en el Cuadro 3.
Análisis filogenético: Para el análisis filogenético se incluyeron secuencias de 89 especímenes, 49 obtenidas del Genbank y las 40 generadas en esta investigación. El alineamiento final de las secuencias alcanzó 1 176 sitios, de los cuales 434 caracteres eran constantes, 236 variables pero no informativos y 506 informativos. La longitud del árbol filogenético con máxima parsimonia fue de 4 585, con índices de consistencia (IC) y retención (IR) de 0.315 y 0.53, respectivamente (Fig. 2). En el dendrograma se presentaron siete clados bien definidos, algunos de los cuales contienen subgrupos internos, así como ramas individuales (Fig. 2).
El clado I albergó un alto número de especímenes (29) recolectados en esta investigación, así como secuencias obtenidas del GenBank que representan especies de los géneros Puccinia, Uromyces, Cumminsiella y Miyagia, razón por la cual se infiere que este grupo corresponde a la familia Pucciniaceae. Adicionalmente, el clado incluyó la secuencia de referencia de Aecidium kalanchoe, lo que puede implicar que este taxón represente el estado anamórfico de una especie de la familia Pucciniaceae. Un aspecto relevante del análisis, es el hecho que aquellos especímenes identificados morfológicamente como pertenecientes a los géneros Chardoniella y Pucciniosira, adscritos a la familia Pucciniosiraceae, fueron incluidos en este clado, al igual que las secuencias de referencia de las especies Pucciniosira pallidula y Dietelia portoricensis. El clado I presentó dos subgrupos medianamente soportados por el análisis de bootstrap. El subgrupo IA, incluye cuatro clados bien soportados estadísticamente: IA-1: corresponde a varios especímenes identificados en este estudio como Chardoniella gynoxidis y Chardoniella sp.; IA-2: conformado por las especies identificadas como Pucciniosira solani y Pucciniosira sp.; IA-3: incluyó la secuencia referencia de Puccinia coronata y las especies identificadas morfológicamente en este estudio como P. coronata y P. striiformis; IA-4: contiene las especies Puccinia peperomiae y una especie del género Maravalia (M. guianensis). Los demás integrantes del subgrupo IA se presentan en ramas individuales o clados con bajo soporte estadístico.
El subgrupo IB presenta dos clados bien soportados, IB-1: incluye las especies Puccinia spegazzinii, mientras que IB-2 contiene las especies P. vernoniae-mollis, P. eupato-rii-colombiani y Pucciniosira pallidula. Los demás integrantes del subgrupo IB corresponden a ramas individuales o clados con bajo soporte estadístico donde están incluidos P. cnici-oleracei, P. hydrocotyles, P. thaliae, U. novissimus (recolectados en este trabajo) y la secuencia de referencia de la especie Dietelia portoricensis, entre otras.
El clado II se ubica en posición basal con respecto al clado I e incluye diferentes secuencias referencia de especies representativas de la familia Pucciniaceae: Gymnosporangium juniperi-virginianae y Puccinia podophylli, además contiene las especies anamórficas Uredo chusqueae y U. baruensis. La secuencia obtenida del GenBank de Kweilingia divina, adscrita a la familia Phakopsoraceae está incluida en este grupo, con un fuerte soporte estadístico y presenta una gran afinidad con el espécimen U. chusqueae.
El clado III está conformado por secuencias de especies representativas de las familias Coleosporiaceae, Cronartiaceae y Pucciniastraceae. Los únicos especímenes del clado colectados en este estudio, fueron identificado morfológicamente como Coleosporium ipomoea, C. vernoniae y una especímen anamórfico determinado como Uredo sp. Caduna de las familias incluidas en este clado presenta un fuerte soporte estadístico en el análisis de bootstrap.
El clado IV representa la familia Phakop soraceae con secuencias de tres géneros Phakopsora, Arthuria y Batistopsora. Además el grupo incluye los especímenes colectados Phakopsora meibomiae y Arthuria sp. El análisis asocia este grupo con la especie Prospodium lippiae, que pertenece a la familia Uropyxidaceae.
El clado V representa los miembros de la familia Phragmidiaceae al incluir secuencias de los géneros Frommeella, Kuehneola, Trachys pora y Gymnoconia.
El clado VI está fuertemente soportado (100%) e incluye dos especies del género Endo raecium, perteneciente a la familia Pileolariacea.
El clado VII está conformado únicamente por dos especies del género Ravenelia (familia Raveneliaceae), además de los especímenes colectados Chrysocelis muehlenbeckiae Chrysocyclus cestri, que representan especie de las familias Mikronegeriaceae y Pucciniaceae, respectivamente.
Además de los clados mencionados, e árbol filogenético presenta una serie de especies dispersas a lo largo del dendrograma, entre las que se destacan el grupo formado por la especie recolectada Uredo zeugites y la secuencia de referencia de Puccinia physalidis; además de las especies Sphenospora kevorkian (Raveneliaceae), asociados al clado I; mientras que las especies Hemileia colombiana y H. vastatrix, no se presentan relacionadas. Finalmente, se destaca que la ubicación taxonómica de las especies Tranzschelia discolor (Uropyxidaceae), Olivea scitula (Chaconiaceae), Melampsoridium betulinum y Melampsora epgea, no es claramente definida por el anális de MP realizado.
Discusión
En este trabajo se realizó un estudio morfológico y filogenético basado en la secuenciación de la subunidad grande (28S) del ADNr de 40 hongos roya recolectados en la región andina de Colombia, estableciéndose sus afinidades con 47 especies (que incluyen especímenes tanto del trópico como de la zona templada), cuyas secuencias se encuentran disponibles en el GenBank y representan al menos un género de cada una de las trece familias propuestas por Cummins & Hiratsuka (2003). Esta investigación se realizó con el ánimo de incluir información referente a hongos roya neotropicales en los estudios recientes que tratan de dilucidar las relaciones evolutivas de los Uredinales y que buscan redefinir su sistema taxonómico.
La validez taxonómica del orden Uredinales (Pucciniales) dentro del Subphylum Puccininiomycotina, ha sido confirmada en dos estudio filogenéticos independientes que utilizaron las secuencias de las subunidades grande y pequeña del ADNr (Aime et al. 2006, Bauer et al. 2006), y que concluyeron que éste representa un grupo monofilético dentro de la Clase Pucciniomycetes; la cual comparte con los ordenes Platygoeales, Heliocobasidiales y Septobasidiales, grupos de los cuales fueronseleccionados los taxones externos empleadosen nuestro estudio filogenético (E. muscicolay S. taxodii) y cuya ubicación en el análisis realizado, ocurrió en forma externa al grupo de los Uredinales.
Tradicionalmente, la taxonomía de los Uredinales se ha basado en el empleo de caracteres morfológicos, cuya ponderación ha variado dependiendo de cada uno de los sistemas planteados. Esta situación ha conducido a propuestas que dividen el orden en dos familias (Dietel 1928) basadas en la estructura de las telioporas (Pucciniaceae: teliosoros erumpentes con teliosporas pediceladas y Melampso- raceae: teliosoros subepidermales, cubiertos y teliosporas sésiles), hasta clasificaciones más complejas que separan el grupo en 13 (Cummins & Hiratsuka 2003), 14 (Cummins & Hiratsuka 1983) ó 16 familias (Buriticá,1999a,b), de acuerdo con la estructura de las teliosporas, el tipo de espermogonio, y en algunos casos las características de los aeciosoros, uredosporas y basidios (Hiratsuka & Hiratsuka 1980). Estudios filogenéticos recientes basados en la secuenciación del ADNr y de algunos genes nucleares (Maier et al. 2003, Wingfield et al. 2004, Aime 2006, Bauer et al. 2006, van Der Merwe et al. 2007) revelan incongruencias a todos lo niveles taxonómicos con la clasificación basada en caracteres morfológicos. Así por ejemplo, Maier et al. (2003) indican que los géneros Puccinia, Pucciniastrum, Thekopsora y Uromyces son claramente polifiléticos, mientras que Aime (2006) encontró que las familias Cronartiaceae, Pucciniastraceae y Puc-ciniosiraceae se presentan como redundantes, mientras que Chaconiaceae y Uropyxidaceae corresponden a taxones no naturales.
En nuestro estudio resultó evidente la separación de Pucciniaceae sensu lato del linaje Melampsoraceae sensu lato (Coleosporaceae, Pucciniastraceae, Cronartiaceae). Sin embargo, el primer grupo se presentó disperso a lo largo del dendrograma, mientras que Melampsoraceae sensu lato sí correspondió a un solo clado (III), aunque Melampsora epigea, la única especie analizada de la familia Melampsoraceae sensu stricto, se ubicó por fuera de ambos grupos, en posición basal. Esta situación fue igualmente encontrada por Maier et al. (2003), quienes proponen que el género Melampsora representa un linaje primitivo del orden Uredinales, caracterizado por su falta de especificidad y la diversidad de relaciones que sus especies establecen con sus hospedantes (Durrieu 1980). Es claro que esta hipótesis sólo puede ser confirmada incluyendo en análisis posteriores un mayor número de especímenes pertecientes a este género y especialmente de hospedantes tropicales ancestrales, tales como los helechos.
El linaje Pucciniaceae sensu lato se caracteriza por presentar especies que cuando son heteroicas, desarrollan aecios sobre angiospermas. Este grupo ha sido subdividido por Cummins & Hiratsuka (2003) con base en el tipo de espermogonio en nueve familias: Mikronegeriaceae, Phakopsoraceae, Chaconiacecae, Uropyxidaceae, Pileolariaceae, Raveneliaceae, Phragmidiaceae, Pucciniaceae y Pucciniosiraceae. En nuestro análisis las siguientes familias corresponden a clados bien definidos con alto soporte estadístico: Pucciniaceae, Phakopsoraceae, Phragmidiaceae, Pileolariacea y Mikronegeriaceae, aunque en algunos casos existen especies que no se agrupan en los clados representativos de dichas familias y que por tanto requieren un tratamiento taxonómico especial, siendo evidente esta situación con algunas especies del género Puccinia. Las familias Uropyxidaceae, Raveneliaceae y Chaconiaceae se presentan como polifiléticas, mientras que Pucciniosiraceae es claramente un taxón redundante con Pucciniaceae. Estas conclusiones del análisis concuerdan con lo encontrado por Aime (2006) quien utilizó un grupo diferente de hongos roya y la combinación de dos regiones ribosomales para su estudio.
El linaje Melampsoraceae sensu lato está conformado por especies de royas que cuando son heteroicas desarrollan su estado aecial sobre plantas gimnospermas (Wingfield et al. 2004). Las familias Coleosporiaceae y Cronartiaceae definidas por Cummins & Hiratsuka (2003), se muestran como clados bien soportados en nuestro análisis, mientras que la familia Pucciniastraceae es polifilética y Melampsoraceae se presenta como un taxón independiente, que requiere un análisis posterior, tal como se mencionó anteriormente.
A continuación se realiza una discusión basada en las familias establecidas por Cummins & Hiratsuka (2003) con relación a los hallazgos de los análisis filogenéticos y morfológicos efectuados en este estudio y con énfasis en los especímenes colectados en la zona andina de Colombia.
Pucciniaceae Chevall
Esta familia comprende el mayor número de hongos roya del orden, con cerca de 7 000 especies y 16 géneros, los géneros Puccinia y Uromyces fueron los más numerosos con 3 000 y 600 especies, respectivamente (Kirk et al. 2001, Cummins & Hiratsuka 2003). El clado que representa esta familia en el análisis filogenético aparece dividido en dos subgrupos (IA y IB), los que a su vez presentan indistintamente especies de Puccinia y Uromyces colectadas en Colombia y en otras regiones del mundo, y se demostró la naturaleza polifilética de dichos géneros. Esta situación fue confirmada por dos estudios recientes realizados con base en secuencias de los genes nucleares EF 1α y β-tub (Van Der Merwe et al. 2007) y de la subunidad grande del ADNr (Maier et al. 2007), en los cuales se analizó un alto número de especies y se determinó que la principal característica morfológica empleada para diferenciar dichos géneros (número de células presentes en las teliosporas), no corresponde a un carácter filogenéticamente informativo. En dichos estudios se encontró que efectivamente las especies tipo de estos géneros (P. graminis y U. appendiculatus) representan linajes diferentes, situación que coincide en esta investigación con la ubicación de U. appendiculatus en un subgrupo diferente a las especies de Puccinia colectadas sobre plantas de la familia Poaceae (P. coronata, P. striiformis), las cuales están estrechamente relacionadas con P. graminis (Maier et al. 2007). En el subgrupo IA, se incluye además un representante del género Cumminsiella y de la especie anamórfica Aecidium kalanchoe. El primero se diferencia del género Puccinia por presentar dos poros por cada célula de las teliosporas, sin embargo la validez filogenética de este género requiere del análisis de un mayor número de especies.
Una confirmación importante de este estudio con respecto a los trabajos de Wingfield et al. (2004), Aime (2006) y Van Der Merwe et al. (2007), corresponde a la redundancia de las familias Pucciniaceae y Pucciniosiraceae. Según Buriticá & Hennen (1980), las royas de esta última familia son derivadas principalmente de especies de ciclo largo del complejo Puccinia-Uromyces, géneros que también resultaron polifiléticos. interesantemente, estos autores en su monografía de Pucciniosireae, sugerían la necesidad de tratar esta familia como una tribu dentro de Pucciniaceae, caracterizada por presentar royas autoicas con ciclo reducido, telioporas en cadena que asemejan aeciosporas y que frecuentemente presentan células intercaladas o estructuras similares a pedicelos. La ubicación de las especies recolectadas pertenecientes a la tribu Pucciniosireae en la parte superior del árbol, sugiere que estas royas son uno de los grupos más evolucionados dentro de los Uredinales incluidos en este análisis, lo cual también es evidenciado por el alto nivel evolutivo de sus hospedantes (ej. Asteraceae: Chardoniella spp). La separación de las especies del género Pucciniosira recolectadas en nuestro estudio con respecto a la especie cuya secuencia se obtuvo del GenBank (P. pallidula) puede ser explicada por las diferencias evidentes entre sus hospedantes, que para nuestro caso corresponden a plantas pertenecientes a los género Solanum y Cestrum endémicas de las zonas altoandinas, mientras que la especie P. pallidula es parásita de Triumfetta semitriloba, una planta de origen más ancestral. De otra parte, la similitud morfológica entre estas royas, puede ser explicada por un proceso de evolución convergente, que hace necesario redefinir los caracteres morfológicos que definen el género Pucciniosira sensu stricto.
Por fuera del clado se ubicó un representante del género Gymnosporangium (Pucciniaceae) el cual tradicionalmente se ha incluido en esta familia con base en la morfología de su espermogonio, aunque presenta otras características que son únicas y que claramente lo diferencian de los demás miembros de Pucciniaceae: estado telial de consistencia gelatinosa desarrollado sobre gimnospermas y estado aecial tipo Roestelia sobre dicotiledóneas frecuentemente de la familia Rosaceae (Cummins & Hiratsuka 2003).
Interesantemente, la especie Puccinia podophylli se presentó asociada con G. juni-peri-virginianae, aunque con un débil soporte estadístico. Este grupo a su vez, conformó un clado con dos especies del género anamórfico Uredo (U. baruensis y U. chusqueae), además de la especie Kweilingia divina, un miembro de la familia Phakopsoraceae. La formación de dicho clado no presenta ninguna justificación desde el punto de vista morfológico y su relación requiere ser redefinida con un mayor número de representantes de los géneros involucrados. De especial interés resultó el hecho que U. chusqueae presentó una alta relación con K. divina, dada la gran afinidad filogenética de sus hospedantes de la familia Poaceae: Guadua angustifolia para K. divina y Chusquea sp. para U. chusqueae.
Finalmente, del análisis filogenético de los miembros de la familia Pucciniaceae recolectados en este estudio, se presentan situaciones puntuales que sin duda brindarán un aporte fundamental desde la perspectiva del neotrópico a la construcción de un sistema taxonómico “más natural” de los hongos roya, pero para lo cual deben ser colectados un mayor número de especímenes. Entre dichas situaciones se destaca la localización de Puccinia oxalidis y P. pittieriana en la posición apical del clado I y la localización de P. smilacis y P. physalidis por fuera del grupo que representa la familia Pucciniaceae, pero en asocio con Gymnoconia peckiana y Uredo zeugites, respectivamente, así como la estrecha asociación entre la especie Maravalia guianensis y Puccinia peperomiae, lo que sin duda merece un análisis futuro, pues morfológicamente estas especies son bastante diferentes.
Phakopsoraceae (Arthur) Cummins & Y. Hiratsuka
Esta familia presenta 13 géneros teliomórficos (Cummins & Hiratsuka 2003) y al menos 10 formas anamórficas (Buriticá & Hennen 1994) de royas en gran diversidad de plantas mono y dicotiledóneas. Se caracterizan por presentar espermogonios del Grupo VI, teliosporas sésiles embebidas en el tejido del hospedante y formadas sobre teliosoros compuestos de una corteza de teliosporas con dos o más células de profundidad (Cummins & Hiratsuka 2003). La familia estuvo representada en el análisis por miembros de los géneros Phakopsora, Batistopsora, Arthuria y Kweilingia. Los tres primeros géneros conformaron el clado IV que presentó un alto soporte en el dendrograma, dentro del cual se ubicó el especímen colectado Arthuria sp., mientras que Kweilingia lo hizó en el clado II. La situación de Kweilingia ya fue discutida anteriormente. En este caso su ubicación por fuera del clado de la familia Phakopsoraceae conduce a inferir que la asociación taxonómica de este género es incierta, aunque su posición en el dendrograma, no soporta la anotación de Thirumalachar & Narasimhan (1951) en el sentido que este hongo no debería ser considerado como una roya, sino como un miembro de los Auriculares. Una interesante evaluación que se deriva de este análisis, es la necesidad de incluir en un estudio posterior royas de esta familia que parasitan pastos tales como aquellas del género Dasturella, pues es posible que dichas especies también se ubiquen por fuera del clado que representa Phakopsoraceae sensu stricto, ya que sus características morfológicas son muy diferentes a aquellas propias de los demás miembros de esta familia.
De especial interés resultaron las diferencias en las secuencias encontradas entre P. pachyrhizi y P. meibomiae, comúnmente conocidas como la roya asiática y americana de la soya, respectivamente, y alrededor de cuya clasificación existe una polémica mundial (Frederick et al. 2002). Nuestros resultados confirman que estas royas no representan la misma especie y que el especímen colectado en Colombia corresponde a P. meibomiae. Morfológicamente esta diferenciación ha sido soportada por estudios basados en sus teliosoros (Ono et al. 1992) y en los trabajos moleculares adelantados por Frederick et al. (2002) y Posada (2008), quienes encontraron que éstas presentan una similitud en las secuencias de las regiones ITS del ADNr de tan sólo 80%, y que su genoma mitocondrial presenta diferencias en tamaño y % G+C (P. pachyrhizi: 31.8 kb, 34.6% vs P. meibomiae: 32.5 kb, 34.9%). Finalmente es importante anotar que el análisis de MP ubicó a esta familia en estrecha relación con Prospodium lippiae, un miembro de la familia Uropyxidaceae caracterizado por formar espermogonios subcuticulares del grupo Phakopsoraceae, pero cuyas teliosporas son claramente diferentes: pediceladas con dos células y con presencia de apéndices basales. Esta relación requiere de un análisis posterior con un mayor número de representates del género Prospodium.
Phragmidiaceae Corda
Esta familia está representada por diez géneros de royas autoicas que parasitan casi exclusivamente plantas de la familia Rosaceae y se caracterizan por producir espermogonios del grupo IV (tipos 6, 8, 10 ó 11) con teliosporas pediceladas con uno a varios septos transversales y desarrolladas sobre telios erumpentes (Cummins & Hiratsuka 2003). Los análisis filogenéticos recientes (Maier et al. 2003, Aime 2006) han confirmado el carácter monofilético de la familia y la cercanía evolutiva entre los géneros Kuehneola y Phragmidium. En nuestro análisis la condición filogenética de esta familia fue igualmente confirmada con base en secuencias de los géneros Gymnoconia, Frommeella, Kuehneola y Trachyspora; sin embargo, el hecho que ninguna especie recolectada de esta familia en Colombia pudo ser secuenciada, hace necesario su abordaje en un futuro estudio. De gran interés será el análisis de diferentes especies del género Gerwasia, el cual afecta plantas del género Rubus, es típicamente tropical y presenta teliosporas de una sola célula, que difieren ampliamente de los demás miembros de esta familia.
Coleosporiaceae Dietel
Esta familia es una de las representantes del suborden Melampsorineae (Aime 2006) que sistemáticamente en los diferentes estudios basados en secuenciación del ADN, se presenta como un linaje filogenético bien soportado, pero cuyos límites familiares no están claramente definidos. Esta situación es evidente cuando se consideran los resultados de los análisis con los dos géneros de la familia Coleosporiaceae incluidos en nuestro estudio: Coleosporium y Chrysomyxa. En este caso, ambos se ubican en el clado III y se presentan individualmente bien soportados, pero con Chrysomyxa más relacionado con los géneros Cronartium y Endocronartium de la familia Cronartiaceae, que con Coleosporium. Esta situación soporta los hallazgos de Maier et al. (2003) y Wingfield et al. (2004) en el sentido que la monofilia de la familia no pudo ser definida y conduce a interpretar que las diferencias morfológicas que se presentan entre ambos géneros: germinación de teliosporas interna (basidiación interna) (Coleosporium) vs germinación de teliosporas que producen basidios externamente (Chrysomyxa), deben ser consideradas más detalladamente en los estudios de este grupo de royas.
Chaconiaceae Cummins & Y. Hiratsuka y Mikronegeriaceae Cummins & Y. Hiratsuka
Morfológicamente la familia Chaconiaceae se caracteriza por presentar espermogonios del grupo VI (tipos 5 ó 7), uredosporas generalmente equinuladas y teliosporas unicelulares, lateralmente libres, sésiles ó pediceladas. Cummins & Hiratsuka (2003) reconocen diez géneros dentro de esta familia, aunque Ono & Hennen (1983) no consideran los géneros Achrotelium, Botryorhiza, Chaconia y Maravalia como pertenecientes a ésta, debido a la presencia de teliosporas pediceladas. Es claro de este estudio y de aquellos adelantados por Wingfield et al. (2004) y Aime (2006) que la válidez taxonómica de la familia Chaconiaceae no es soportada filogenéticamente, siendo evidente la necesidad de clarificar la afinidad de algunos de sus géneros con la familia Mikronegeriaceae; familia ésta que sólo estuvo representada por la especie Chrysocelis muechlenbeckiae y cuya ubicación en el dendrograma correspondió a un clado compartido con Chrysocyclus cestri (Pucciniaceae) y dos especies de Ravenelia (Raveneliaceae).
La afinidad del género Hemileia con esta familia es igualmente problemática, pues ya desde la mitad del siglo pasado Thirumalachar & Mundkur (1949) habían sugerido que este taxón estaba relacionado con el género Blastospora, hoy en día considerado de la familia Mikronegeriaceae (Cummins & Hiratsuka2003). Esta cercana asociación fue recientemente confirmada por Aime (2006), quien con base en análisis del ADNr sugiere que Hemileia y al menos una especie del género Maravalia (M. cryptostegiae) deberían ser ubicadas en Mikronegeriaceae, la que además representa un grupo ancestral dentro del orden Uredinales. Esta situación se vió reflejada en nuestro estudio mediante MP. El análisis además no permitió establecer una cercana relación entre H. vastatrix (agente causal de la roya del café) y H. colombiana (roya de Apocynaceae); así como tampoco fueron definidas afinidades entre éstas royas y las otras especies estudiadas de la familia Chaconiacae (Olivea scitula y Maravalia guianensis); pues la primera especie aparece en posición basal en el dendrograma, mientras que M. guianensis se ubicó en el clado IA, que representa un linaje de la familia Pucciniaceae.
A partir de los resultados de esta investigación, que incluyó un alto número de hongos roya representantes de diferentes géneros, se propone priorizar la continuación de este estudio con base en el análisis filogenético de los siguientes taxones:Gerwasia, Hemileia, Phragmidium, Prospodium, Puccinia y Uromyces. Dichos grupos contienen gran cantidad de royas presentes en el trópico que requieren ser estudiadas más detalladamente.
Agradecimientos
Esta investigación se realizó gracias al apoyo económico de la dirección de investigaciones de la Universidad Nacional de Colombia sede Medellín a través del proyecto 20201005428. La identificación taxonómica de los hospedantes se realizó con apoyo de Jorge Pérez del Herbario Medel y el análisis filogenético con la colaboración de Andrés López Rubio y Sandra Uribe Soto del Grupo de sistemática molecular UNAL-MED. Se agradece a Mauricio Salazar Yepes por la revisión crítica del manuscrito.
Referencias
Aime, M.C. 2006. Toward resolving family-level relation-ships in rust fungi (Uredinales). Mycoscience 47: 112-122. [ Links ]
Aime, M.C., M.P. Brandon, D.A. Henk, E.M. Frieders, R.H. Nilson, M. Piepenbring, D.J. Mclaughlin, L.J. Szabo, D. Begerow, J.P. Sampaio, R. Bauer, M. Weib, F.Y. Oberwinkler & D. Hibbert. 2006. An overview of the higher level classification of Pucciniomyco-tina based on combined analyses of nuclear large and small subunit rDNA sequenses. Mycologia 98: 896-905. [ Links ]
Bauer, R., D. Begerow, J.P. Sampaio, M. Weiß & F. Oberwinkler. 2006. The simple-septate basidiomyce-tes: a synopsis. Mycol. Progr. 5: 41-66. [ Links ]
Blackwell, M., D. Hibbert, J.W. Taylor & J.W. Spatafora. 2006. Research Coordination Networks: a phylogeny or kingdom Fungi (Deep Hypha). Mycologia 98: 829-837. [ Links ]
Buriticá, P. 1991. Familias del orden Uredinales con ciclo de vida completamente reducido. Rev. Acad. Col. Cienc. 18: 131-148. [ Links ]
Buriticá, P. 1994. Cambios taxonómicos y nuevos registros de Uredinales de la flora andina. Rev. i.C.N.E. 5: 173-190. [ Links ]
Buriticá, P. 1999a. Familia Phakopsoraceae (Uredinales) en el Neotrópico III, géneros Batistopsora y Phakopsora. Rev. Acad. Col. 23: 272. [ Links ]
Buriticá, P. 1999b. Familia Phakopsoraceae (Uredinales) en el Neotrópico IV, Géneros Cropssopsora, Cerotelium, Phragmidiella y Catenulopsora. Rev. Acad. Col. 23: 407. [ Links ]
Buriticá, P. 2000. Adaptación al ambiente de Uredinales neotropicales. O Biol. 62: 127-141. [ Links ]
Buriticá, P. 2001. Descubriendo ancestros de los Uredina-les. Rev. Acad. Col. Cien. 25: 395-401. [ Links ]
Buriticá, P. 2003a. Centros naturales de diversificación en el orden Uredinales (Fungi, royas). Rev. Fac. Nal. Agr. Medellín 56: 1999-2019. [ Links ]
Buriticá, P. 2003b. Estado del conocimiento universal sobre el orden Uredinales (Fungi, royas). Rev. Fac. Nal. Agr. Medellín 56: 1813-1838. [ Links ]
Buriticá, P. & J. Hennen. 1980. Familia Phakopsoraceae (Uredinales). Géneros anamórficos y teliomórficos. Rev. Acad. Colomb. Cienc. Ex. Fis. Nat. 19: 47-62. [ Links ]
Buriticá, P. & J. Hennen. 1980. Pucciniosireae (Uredi-nales, Pucciniaceae). Flora Neotropica Monograph 24: 1-50. [ Links ]
Buriticá, P. & J. Hennen. 1994. Familia Phakopsoraceae (Uredinales). 1. Géneros anamórficos y teliomórficos. Rev. Acad. Colomb. Cienc. Ex. Fis. Nat. 19:47-62. [ Links ]
CABI, CBS & Landcare Research. 2008. Index Fungorum. (Consultado: Diciembre 2007, http://www.indexfungorum.org). [ Links ]
Cummins, G. 1940. The genus Prospodium (Uredinales). Lloydia 3: 1-78. [ Links ]
Cummins, G. 1971. The rust fungi of cereals, grasses and bamboos. Springer-Verlag, Nueva York, EEUU. [ Links ]
Cummins, G. 1978. Rust fungi on legumes and composites in North America. University of Arizona Tucson, Tucson, EEUU. [ Links ]
Cummins, G. & Y. Hiratsuka. 1983. Illustrated genera of rust fungi. American Phytophatological Society, San Pablo, EEUU. [ Links ]
Cummins, G. & Y. Hiratsuka. 1991. Illustrated genera of rust fungi. American Phytophatological Society, San Pablo, EEUU. [ Links ]
Cummins, G. & Y. Hiratsuka. 2003. Illustrated general of rust fungi. American Phytophatological Society, San Pablo, EEUU. [ Links ]
Dietel, P. 1928. Hemibasidii (Ustilaginales and Uredina-les), p 24-98. In A. Engler & K. Plantl (eds). Die Natürlichen Pflanzenfamilien, vol 2. Engelmann, Leipzig, Alemania. [ Links ]
Durrieu, G. 1980. Phylogeny of Uredinales on Pinaceae. Rep. Tottori Mycol. inst. 18: 283-290. [ Links ]
Felsenstein, J. 1985. Confidence limits on phylogenies: an approach using the bootstrap. Evolution 39: 783-791. [ Links ]
Frederick, R.D., C.L. Snyder, G.L. Peterson & M.R. Bonde. 2002. Polymerase chain reaction assays for the detection and discrimination of the soybean rust pathogens Phakopsora pachyrhizi and P. meibomiae. Phytopathology 92: 217-227. [ Links ]
Gaumann, E. 1949. Die Pilze. Grundzüge ihrer Entwicklungsgeschichte und Morphologie. Birkhauser, Basilea, Suiza. [ Links ]
Guadet, J., J. Julien & J. Francois. 1989. Phylogeny of some Fusarium species, as determined by largesubunit rRNA sequence comparison. Mol. Biol. Evol. 6: 227-242. [ Links ]
Hahn, M. 2000. The rust fungal, p. 267-306. In J. Krons-tand (ed.). Fungal pathology. Kluwer, Holanda. [ Links ]
Hawksworth, D.L., P.M. Kirk, B.C. Sutton & D.N. Pegler. 2001. Ainswork & Bisby´s dictionary of the fungi. 8th ed. int. Mycol. inst., CAB int., Egham, Reino Unido. [ Links ]
Hennen, J., M. Hennen & M. Figueiredo. 1982. indice das ferrugens (Uredinales) do Brasil. Arq. inst. Biol. (Sao Paulo) 49: 1-201. [ Links ]
Hennen, J., M. Figueiredo, A. De Carvalho & P.G. Hen-nen. 2005. Catalogue of the species of plant rust fungi (Uredinales) of Brazil. (Consultado: Octubre 2007, http://www.jbrj.gov.br/publica/uredinales/Brazil_Catalogue1drevisado.pdf). [ Links ]
Hiratsuka, Y. & N. Hiratsuka. 1980. Morphology of spermogonia and taxonomy of rust fungi. Rep. Tottori Mycol. inst. 18: 257-268. [ Links ]
Hopple, J. & R. vilgalys. 1999. Phylogenetic relationships in the mushroom genus Coprinus and darkspored allies based on sequence data from the nuclear gene coding for the large ribosomal subunit RNA: divergent domains, outgroups, and monophyly. Mol. Phylogenet. Evol. 13: 1-19. [ Links ]
Kirk, P.M., P.F. Cannon, J.C. David & J.A. Stalpers. 2001. Dictionary of the fungi. CABi, Wallingford, Reino Unido. [ Links ]
The New York Botanical Garden Herbarium. 2003. Catalog of Rust Types. (Consultado: Abril 2008, http://www.nybg.org/bsci/hcol/rust). [ Links ]
Maier, W., D. Begerow, M.Y. Wei & F. Oberwinkler. 2003. Phylogeny of the rust fungi: An approach using nuclear large subunit ribosomal DNA sequences. Can. J. Bot. 81: 1-12. [ Links ]
Maier, W., B.D. Wingfield & M. Mennicken. 2007. Polyphyly and two emerging lineages in the rust genera Puccnia and Uromyces. Mycol. Res. 176-185. [ Links ]
Ono, Y., P. Buriticá & J.F. Hennen. 1992. Delimitation of Phakopsora, Physopella and Cerotelium and their species on Leguminosae. Mycol. Res. 96: 825-850. [ Links ]
Ono, Y. & J.F. Hennen. 1983. Taxonomy of the Chaconiaceous genera (Uredinales). Trans. Mycol. Soc. Jpn. 24: 369-402. [ Links ]
Pardo-Cardona, v. 1999. Notas técnicas especies de Ure-dinales (Royas) con rara formación del estado teliomórfico en Colombia. Rev. Fac. Nal. Agr. Medellín 52: 755-764. [ Links ]
Pardo-Cardona, v. 2001. Historia, estado actual y perspectivas de la investigación de los Uredinales en Colombia. Rev. Fac. Nal. Agr. Medellín 54: 1333-1350. [ Links ]
Posada, M.L. 2008. Soybean rust, a rising star in phytopatho-logy. (Consultado: Abril 2008, http://www.osti.gov/bridge/servlets/purl/860744-7ClNx8/860744.PDF). [ Links ]
Salazar, M. 2002. Uredinales (royas) en la zona cafetera colombiana. Tesis Maestría, Universidad de Caldas, Manizales, Colombia. [ Links ]
Salazar, M., V. Pardo-Cardona & P. Buriticá. 2007. Especies de Colombia, Ecuador y Perú pertenecientes al género Gerwasia Raciborski del orden Uredinales. Caldasia 29: 105-120 [ Links ]
Sugiyama, J. 1998. Relatedness, phylogeny, and evolution of the fungi. Mycoscience 39: 487-511. [ Links ]
Swofford, D.L. 1998. PAUP: Phylogenetic analysis using parsimony (* and other methods). versión: 4. Sinauer Associates, Sunderland, EEUU. [ Links ]
Thirumalachar, M.J. & B.B. Mundkur. 1949. Genera of rust ii. ind. Phytopathol. 2: 65-101. [ Links ]
Thirumalachar, M.J. & M.J. Narasimhan. 1951. Critical notes on some plant rusts. iii. Sydowia 5: 476-483. [ Links ]
Van Der Merwe, M., L. Ericson, J. Walker, P.H. Thrall & J.J. Burdon. 2007. Evolutionary relationships among species of Puccinia and Uromyces (Pucciniaceae, Uredinales) inferred from partial protein coding gene phylogenies. Mycol. Res. 111: 163-175. [ Links ]
Vogler, D. & T. Bruns. 1998. Phylogenetic relationships among the pine stem rust fungi (Cronartium and Peridermium spp.). Mycologia 99: 244-257. [ Links ]
Wingfield, B., L. Ericson, T. Szaro & J. Burdon. 2004. Phylogenetic patterns in the Uredinales. Australas. Plant Pathol. 33: 327-335. [ Links ]
Zuluaga, C., P. Buriticá & M. Marín. 2009. Generalidades de los Uredinales (Fungi: Basidiomycota) y de sus relaciones filogenéticas. Acta Biol. Colomb. 14: 39-54 [ Links ]
Correspondencia a: Catalina Zuluaga & Mauricio Marín. Universidad Nacional de Colombia sede Medellín, Laboratorio de Biología Celular y Molecular, Cra 64 x Calle 65, Autopista Norte, Medellín, Colombia; catazuluaga81@gmail.com, mamarinm@unal.edu.co
Pablo Buriticá. Universidad Nacional de Colombia sede Medellín, Departamento de Ciencias Agronómicas, Cra 64 x Calle 65, Autopista Norte, Medellín, Colombia; pburitica@unal.edu.co
Recibido 16-IV-2010. Corregido 10-IX-2010. Aceptado 26-X-2010.